Elucigene QST*R-21 Euplex Brugervejledning
|
|
|
- Elisabeth Bagge
- 10 år siden
- Visninger:
Transkript
1 Elucigene QST*R-21 Euplex Brugervejledning Produkt Størrelse Katalogkode Elucigene QST*R-21 Euplex 10 test ANE21BX Til in vitrodiagnostisk brug Fremstillet af: Elucigene Diagnostics Citylabs Nelson Street Manchester M13 9NQ, Storbritannien For salg, kundeservice og teknisk support: Tlf.: F: +44 (0) Fax: F: +44 (0) Elucigene Diagnosticser handelsbetegnelsen tilhørende Delta Diagnostics (UK) Limited., et selskab der er indregistreret i England og Wales, registreringsnummer ANE21BYDA 002 OKT-2015 Side 1 af 40
2 Elucigene QST*R-21 Euplex Tilsigtet anvendelse QST*R-21 Euplex er et supplerende sæt, der er beregnet til brug sammen med QST*R eller QST*Rplusv2 til den rutinemæssige, kvantitative in vitro-diagnose af trisomier i forbindelse med kromosom 21 (Downs syndrom). Assay'et er beregnet til supplerende kromosomtestning, når der er behov for det, eller til bekræftelse af positive resultater. Metoden, som disse sæt benytter, er teknikken QF-PCR (Quantitative Fluorescence-Polymerase Chain Reaction) (kvantitativ fluorescenspolymerasekædereaktion). Produkterne er beregnet til at blive brugt på DNA, der er udtaget fra enten fostervand eller moderkageprøver, som er taget under en fostervandsundersøgelse. Den tilsigtede målpopulation er gravide kvinder, der via enten biokemiske eller ultralydsdiagnostiske procedurer vurderes at have stor risiko for at bære et angrebet foster eller vurderes til at være i risikogruppe på grund af enten tidligere familieanamnese eller fødealder. Produktet er beregnet til at blive brugt sammen med andre diagnostiske procedurer for at understøtte eller udelukke den foreslåede kliniske diagnose. Produktet er udelukkende til professionel brug i et molekylært eller cytogent laboratoriemiljø. Resume og forklaring Risikoen for at føde et barn med Downs syndrom øges signifikant med moderens alder fra ca. 1:1600 i alderen til 1:200 i alderen 35 og 1:19 i alderen 45 og ældre. Gravide kvinder tilbydes rutinemæssigt screening for Downs syndrom i graviditetens første trimester. En standardtest er den såkaldte OSCAR -test, One Stop Clinical Assessment of Risk (en spids for klinisk vurdering af risiko), der foretages mellem 10 og 13½ uge under graviditeten. Denne kombinerer to biokemiske markører, frit beta hcg (human Chorionic Gonadotrophin) og PAPP-A (Pregnancy Associated Plasma Protein-A) med måling af tykkelsen af fosterets nakkefold (nakkefoldsscanning) (1). Kombinationen af resultaterne af disse tre test giver et generelt risikotal. Kvinder, som identificeres som at have øget risiko for at føde et barn med Downs syndrom, tilbydes derefter fostervandsundersøgelse for at teste direkte for abnormitet. En fostervandsundersøgelse er en invasiv test, der indebærer indføring af en kanyle i fosterhinden omkring fosteret under ultralydsvejledning. Der udtages og testes en lille prøve, typisk ml, af fostervand med fosterceller. Downs syndrom blev opkaldt efter Dr. John Langdon Down i 1866, men er beskrevet tidligere. Det forårsages af trisomi for alle eller en del af kromosom 21 (2). Personer med Downs syndrom har foruden kognitiv funktionsnedsættelse af varierende grad typisk et antal fælles træk, herunder hypotoni (nedsat muskelkraft), fremstående tunge, mandelformede øjne, der skyldes en epikantisk fold, opadgående palpebrale fissurer, enkelt fure i hånd og ekstremiteter, der er kortere end normalt. De har endvidere øget risiko for medfødte hjertedefekter og for senere i livet at udvikle en form for Alzheimers sygdom. ANE21BYDA 002 OKT-2015 Side 2 af 40
3 Procedureprincip Metoden, som Elucigene QST*R-sættene anvender, er teknikken QF-PCR (Quantitative Fluorescence- Polymerase Chain Reaction) (kvantitativ fluorescenspolymerasekædereaktion) (3-7). Ved anvendelse af PCR-amplifikation rettes fluorescensfarvemærkede primere mod højpolymorfe områder af DNAsekvens, der kaldes STR (short tandem repeats korte tandemgentagelser), som er placeret på kromosomerne af interesse. Hver målrettet STR-markør er specifik for det kromosom, den sidder på, og derfor kan STR-markørens kopinummer være diagnostisk for kromosomets kopinummer. Der er blevet valgt informative STR-markører, der påviser en høj heterogenitet, således at kopinummeret let kan bestemmes. En normal diploid prøve har det normale komplement af to af hver af de somatiske kromosomer. To alleler af en kromosomspecifik STR-markør bestemmes derfor af QF-PCR-teknikken som to spidser i et 1:1-forhold. Observationen af en ekstra STR-allele som enten et mønster med tre spidser i et 1:1:1-forhold eller et mønster med to spidser i et 2:1- eller 1:2-spidsforhold er diagnostisk for forekomsten af en ekstra sekvens, som igen kan repræsentere et ekstra kromosom, som ved en trisomi. QF-PCR-teknikkens amplificerede produkter analyseres kvantitativt på en kapillærelektroforesegenetisk analyzer for at bestemme de analyserede STR-markørers kopinummer. Advarsler og forholdsregler 1. Den normale DNA-kontrol, der medfølger i sættene, er testet uafhængigt og konstateret negativ for Hepatitis B virus (HBV), Hepatitis C virus (HCV) og human immundefektvirus (HIV) 1 og Vær forsigtig ved håndtering af materiale af human oprindelse. Alle prøver bør anses som potentielt smittefarlige. Ingen testmetode kan give fuld sikkerhed for, at HBV, HCV, HIV eller andre smitstoffer ikke er til stede. 3. Håndtering af prøver og testkomponenter, deres brug, opbevaring og bortskaffelse skal ske i overensstemmelse med de procedurer, der er defineret af de relevante nationale bestemmelser og regulativer vedrørende biologisk risikomateriale. 4. I overensstemmelse med aktuel god laboratoriepraksis bør laboratorier behandle deres egne interne kvalitetskontrolprøver af kendt genotype i hvert assay, så procedurens validitet kan vurderes. 5. Hvis æsken med kittet er beskadiget, kan indholdet være beskadiget. Anvend ikke kittet, og kontakt kundeservice. ANE21BYDA 002 OKT-2015 Side 3 af 40
4 Symboler anvendt på etiketter Symbolerne anvendt på alle etiketter og emballage er i overensstemmelse med den harmoniserede standard ISO Producent Antal test Se brugervejledning X C Opbevares under den angivne temperatur Anvendes før den angivne dato Katalogkode Partinummer Medicinsk udstyr til in vitro diagnostik ANE21BYDA 002 OKT-2015 Side 4 af 40
5 Materialer der følger med Opbevar alle komponenter under -20 C. Elucigene QST*R-21 Euplex IVD-sættet indeholder: x 100µl reaktionsblanding (TA) x 50µl Kontrol DNA (DC) Rækker til 10 test. Klargøring af sæt og opbevaring Når sættet er åbnet, anbefales det, at dispensere reaktionsblandingen over i et 0,2 ml hætteglas i kvanta på 10 µl og frossen ved -20 C. Sørg for at indholdet i hætteglasset er tøet helt op og blandet inden dispensering. Kontrol-DNA'et skal være frosset ved -20 C. Påkrævede men ikke medfølgende materialer Generelt Forbrugsvarer i laboratoriet handsker, mikrofugeglas med skruelåg: 0,2 ml hætteglas eller mikrotiterplader anbefalet af producenten af den anvendte termiske cycler; pipettespidser. Laboratorieudstyr præcisionspipetter (2 sæt: 1 til håndtering før amplifikation og 1 til håndtering efter amplifikation: helst positive displacement-pipetter), beskyttelsestøj, vortex-mixer, mikrofuge, centrifuge til mikrotiterplade med 96 brønde. DNA-ekstraktion Forberedelse af DNA InstaGene Matrix (Bio-Rad Laboratories, katalognr ), sterilt deioniseret vand. PCR-amplifikation Den termiske variator skal kunne rumme mikrotiterplader med 96 brønde eller 0,2 ml hætteglas med en temperaturnøjagtighed på +/-1 C mellem 33 C og 100 C og en statisk temperaturkonstans på +/- 1 C. QST*R-21 Euplex er valideret på og har udvist en ydelse svarende til specifikationen på følgende termiske variatorplatforme: Life Technologies GeneAmp 9700 (som kører i standardmodus) Life Technologies Veriti Dx (som kører i standardmodus) Life Technologies Veriti Dx (som kører i 9700-simuleringsmodus) Life Technologies Proflex Dx (som kører i standardmodus) ANE21BYDA 002 OKT-2015 Side 5 af 40
6 Kapillærelektroforese Kapillærelektroforese GeneScan 500 LIZ størrelsesstandard (ABI katalognr ), POP-7 polymer (ABI katalognr ), DS-33 (farvestofsæt G5) matrixstandard (ABI katalognr ), 10x Genetic Analyzer Buffer (ABI katalognr ) og Hi-Di-formamid (ABI katalognr ). Applied Biosystems ABI 3130 og 3500 genetic analyzere (med aktuel dataindhentnings-software), 36 cm kapillærarray (50 cm kapillærarray for 3500 genetic analyzer), 96-brønds optiske plader, 96-brønds septa, 96-brønds kassetter. Data-analyse Der kræves én af følgende data-analysesoftwarepakker: GeneMapper 3.7 (Applied Biosystems Inc.) eller nyere eller GeneMarker 1.65 (SoftGenetics LLC) eller nyere. Yderligere Elucigene QST*R-dokumentation Denne brugervejledning omfatter et grundlæggende afsnit om fortolkningen af opnåede resultater foruden en vejledning til softwareanalyse med både GeneMapper- og GeneMarker-pakker. Der findes en supplerende vejledning til fortolkning med eksempler og glossar på Elucigene-hjemmesiden: Prøvetagning og opbevaring Der skal anvendes prøver af moderkage (CV Chorionic Villus) eller fostervand (AF Amniotic Fluid). Prøveudtagningsudstyr har til tider vist sig at være skadeligt for integriteten af visse analytter og kan derfor interferere med nogle metodeteknologier. Det anbefales, at hver bruger sikrer, at det valgte udstyr anvendes i overensstemmelse med producentens anvisninger, og at både prøvetagningsudstyr og DNA-klargøringsmetoder er forenelige med denne test. ANE21BYDA 002 OKT-2015 Side 6 af 40
7 DNA-ekstraktion Elucigene QST*R-sættene er valideret på InstaGene-matrixmetoden med DNA-ekstraktion og kan udføres i et enkelt reagensglas, hvilket gør det unødvendigt at overføre fra reagensglas til reagensglas. Der er vist andre ekstraktionsmetoder for at opnå ligeså pålidelige resultater f.eks. Qiagen QIAampsæt. InstaGene-metoden til DNA-ekstraktion er beskrevet herunder. InstaGene-ekstraktionsmetode Fostervand (AF Amniotic Fluid) Der skal anvendes ca. 1-2 ml fostervand. Moderkage (CV Chorionic Villus) CV-prøver skal rengøres omhyggeligt for at fjerne eventuel påsiddende livmoderslimhinde. Det er vigtigt at teste celler fra mere end et område af prøven og at der er repræsenteret celler fra den mesenchymale kerne. En lille alikvot med cellesuspension, der er forberedt til konventionel opsætning af cellekultur, anbefales til QST*R-analyse. Dette sikrer, at QST*R-resultatet opnås fra den samme cellepopulation, som den der anvendes til analyse af karyotypen. 1. Resuspender InstaGene-matricen på det magnetiske røreapparat ved mediumhastighed i mindst 5 minutter. 2. Centrifuger prøven (AF eller CV) ved g i 1 minut for at pellettere cellerne. 3. Fjern prøverne fra centrifugen og efterse pelleten for blodpletter. Noter procentdelen af blodpletter, hvis de forekommer. 4. Fjern og bortskaf forsigtigt supernatanten fra pelleten, og kontroller, at pelleten ikke er kompromitteret. Lad ca µl supernatant være tilbage for at resuspendere pelleten. 5. Bland prøven grundigt på vortexmixer. 6. Fortsæt til trin 7, hvis der observeres mere end 50 % blodpletter. Fortsæt til trin 8, hvis der observeres mindre end 50 % blodpletter. 7. Tilsæt 200 µl sterilt deioniseret vand til cellepelleten. Bland grundigt på vortexmixer. Centrifuger ved g i 1 minut. Fjern supernatanten, og lad µl supernatant være tilbage for at resuspendere pelleten. Bemærk: Dette ekstra vasketrin er med til at lyse de røde blodceller og fjerne hæm, der kan hæmme PCR. 8. Tilsæt 200 µl InstaGene-matrix fra trin 1 til prøverne med en pipettespids med en stor indvendig diameter, som f.eks µl. Bemærk: Til optimimering af ekstraktionsprotokollen kan den tilsatte mængde InstaGenematrix (Chelex-100 resin) varieres med 100 µl InstaGene-matrix til små AF-cellepelleter (knap synlige) eller 300 µl til store pelleter (der dækker bunden af reagensglasset), CV og vævsprøver. Noter den mængde InstaGene-matrix, der er tilsat hver prøve. 9. Bland prøverne omhyggeligt på vortexmixer, og inkuber ved 100 C i 8 minutter i en varmeblok eller et vandbad. 10. Bland igen omhyggeligt på vortexmixer ved høj hastighed i 10 sekunder. 11. Centrifuger prøverne ved g i 3 minutter. Supernatanten indeholder den udtagne DNA. 12. Fortsæt til opsætning af PCR, eller opbevar den udtagne DNA ved -20 C, indtil det er påkrævet. ANE21BYDA 002 OKT-2015 Side 7 af 40
8 DNA-koncentration Det anbefales, at alternative metoder til udtagning af DNA og prøvetyper nøje evalueres med Elucigene QST*R-testen, inden resultaterne anvendes til diagnostik. Ved optimale PCR-forhold, og når der anvendes de anbefalede prøveinjektionsindstillinger*, der er anført i kapillærkolonne-køremodulet (side 11), opnås acceptable resultater konsekvent med input- DNA-mængder på 1,25 ng til 10 ng. *Bemærk: Prøveinjektionsindstillinger kan ændres, så de passer til den mængde amplikon, der produceres under PCR-reaktionen, der kan variere med den mængde input-genomisk DNA, der tilføres. Der kan tilføres mindre amplikon til den kolonne, der skal analyseres, ved at reducere injektionstiden. Omvendt kan der tilføres mere amplikon til den kolonne, der skal analyseres, ved enten at øge injektionens tid eller spænding. Tidligere amplificerede prøver kan injiceres igen flere gange til ny analyse. ANE21BYDA 002 OKT-2015 Side 8 af 40
9 Testprotokol Amplifikationsprocedure Bemærk: For at minimere risikoen for kontaminering skal trin 3-5 udføres i et område uden DNA. Sørg desuden for at undgå kontaminering med PCR-produktet. 1. Programmer den termiske variator til en éttrins cyklus, som aktiverer DNA-polymerasen ved 95 C i 15 minutter, forbundet med et amplifikationscyklusprogram på 30 sekunder ved 95 C (denaturering), 1 minut og 30 sekunder ved 59 C (annealing) og 1 minut og 30 sekunder ved 72 C (udvidelse) i 26 cyklusser. Dette bør forbindes med en 30-minutters tidsforsinkelsesfil ved 72 C (udvidelse) i den endelige cyklus. Enzymaktivering Sekvensering Endelig Udvidelse 95 o C 95 o C 15 min. 30 sek. 72 o C 72 o C 59 o C 1 min. 30 sek. 30 min. Omgivelsestemperatur 1 min. 30 sek. 26 cyklusser 2. Der skal inkluderes en negativ (vand-) kontrol i hver PCR-kørsel. Det kan også være relevant at medtage andre kontrolmuligheder, f.eks. positiv normal (DNA-kontrol medfølger) og positiv trisomikontrol (DNA medfølger ikke). 3. Optø et tilstrækkeligt antal hætteglas med præalikvotet QST*R-21-reaktionsblanding til antallet af prøver og kontroller, der skal køres (se note under Materialer der følger med), og centrifuger hætteglassene ved g i 10 sekunder. 4. Anvend separate pipettespidser, og tilsæt 2,5 µl test-dna i et prøvehætteglas med 10 µl QST*R-21-reaktionsblanding, og bland ved at pipettere op og ned. Gør dette for alle prøver, der skal testes. 5. Der må ikke tilføjes DNA i PCR-hætteglasset til negativ kontrol. Tilsæt i stedet 2,5 µl sterilt destilleret vand. Bemærk: Der skal udvises forsigtighed for ikke at kontaminere PCR-reaktionen med noget som helst InstaGene-resin. 6. Centrifuger hætteglassene kort, indtil al væske er i bunden af hvert hætteglas. 7. Sæt alle hætteglas godt fast i den termiske variatorblok. Start 95 C-aktiveringsprogrammet efterfulgt af amplifikationsprogrammet (se trin 1). 8. Når amplifikationsprogrammet er fuldført, kan prøverne opbevares ved stuetemperatur natten over eller ved 2-8 C i op til 7 dage inden analyse med kapillærelektroforese. ANE21BYDA 002 OKT-2015 Side 9 af 40
10 Kapillærelektroforese Det anbefales, at hver bruger sikrer, at det valgte udstyr anvendes i overensstemmelse med producentens anvisninger, og at prøvetagningsudstyret er foreneligt med denne test. I denne sammenhæng er de vigtigste parametre polymeren og kapillærarrayet. Der kan opnås optimale resultater med følgende kapillærelektroforeseforhold på en ABI3130- eller ABI3500-genetic analyzer. 1. Kombiner 6,85 μl i størrelsesstandard med 250 μl Hi-Di formamid, og bland grundigt (tilstrækkelig blanding til 16 brønde). Dispenser 15 µl blanding ned i det påkrævede antal brønde på en 96-brøndes optisk plade.* 2. Tilsæt 3 µl testprøve-pcr-produkt i den størrelsesstandardblanding (fra trin 1), der allerede er dispenseret ned i pladen, og bland med pipetten. Forsegl pladen. 3. Denaturer det PCR-produkt, der er dispenseret ned i den optiske plade på en termisk variator, med følgende parametre: 94 C i 3 minutter forbundet med 4 C i 30 sekunder. 4. Centrifuger pladen ved g i 10 sekunder for at fjerne eventuelle bobler i brøndene, og sæt den i genetic analyzer. *Bemærk: Det er vigtigt, at ikke-anvendte brønde (dvs. brønde der ikke er fyldt med DNA) også fyldes med Hi-Di formamid for at sikre, at kapillærerne ikke tørrer ud. ANE21BYDA 002 OKT-2015 Side 10 af 40
11 Post-PCR data-analyse ABI3130 GENETIC ANALYZER Opret et prøveark med 3130 dataindsamlingssoftwaren med følgende indstillinger: Sample Name (prøvenavn): Dette skal være det samme prøvespecifikke navn eller nummer. Run Owner (kørselsejer): Vælg laboratoriets standardejer. Kørselsprotokol: QSTR (indeholder QST*R 3130-kørselsmodul se herunder).* *Bemærk: Det er nødvendigt at oprette et kørselsmodul, der angiver instrumentindstillingerne, og efterfølgende tildele dette til en kørselsprotokol, hvor Dye Set (farvestofsættet) G5 er blevet valgt. For yderligere oplysninger om oprettelsen af kørselsmoduler henvises der til instrumentets brugervejledning RUN MODULE (KØRSELSMODUL) TIL POP7-POLYMER 36 cm kapillærmodul: QSTR # Parameternavn Værdi Område 1 Ovntemperatur 60 int grader C 2 Poly_fill_Vol trin 3 Aktuel stabilitet 5,0 int uamp 4 PreRun_Voltage 15, kvolt 5 Pre_Run_Time sek. 6 Injection_Voltage 3, kvolt 7 Injection_Time sek. 8 Voltage_Number_of_Steps nk. 9 Voltage_Step_Interval sek. 10 Data_Delay_Time sek. 11 Run_Voltage 15, kvolt 12 Run_Time sek. ANE21BYDA 002 OKT-2015 Side 11 af 40
12 ABI3500 GENETIC ANALYZER Der skal oprettes en QST*R-instrumentprotokol, som herefter kan bruges til hver QST*R-kørsel. Opret QST*R-instrumentprotokollen via 3500 Instrument Protocols Library (instrumentprotokolbiblioteket). Sørg for at følgende er valgt: Run Module (kørselsmodul): FragmentAnalysis50_POP7 Indlæs de indstillinger, der er angivet i billedet nedenfor: Opret en prøveplade for at køre prøverne ved at klikke på Create Plate from Template (opret plade fra skabelon) på Dashboard (instrumentbrættet), og sørg for, at den korrekte instrumentprotokol for QSTR er blevet tildelt (se ovenfor). Analyse og fortolkning af resultater Det anbefales, at hvert laboratorium udvikler sine egne fortolknings- og rapporteringsprocedurer og kriterier. Retningslinjer for den bedste praksis for QF-PCR er dokumenteret af Storbritanniens Clinical Genetic Science og er tilgængelig til reference på: PCR-produkter observeres som et 5-farvestofmærket system ved brug af filtersæt G5. Filtersæt G5 påviser de 6-FAM (blå), VIC (grønne), NED (gule) og PET (røde) mærkede fragmenter plus markøren Size Standard (størrelsesstandard), der er mærket med LIZ (orange) på et elektroforetogram og i GeneMapper- eller GeneMarker-programmet. En vejledning til fortolkning findes på Elucigene-hjemmesiden: ANE21BYDA 002 OKT-2015 Side 12 af 40
13 Vigtig bemærkning: Forskellige kombinationer af instrument, polymer og størrelsesstandard kan forårsage, at størrelsessøgningen varierer en smule. Under validering af sættet skal brugerne kontrollere, at standard-bin-indstillingerne resulterer i nøjagtig spidsmærkning, og justere dem, hvis det er nødvendigt. Kontakt teknisk support ([email protected]) for at få hjælp i tilfælde af eventuelle problemer. Generelle analyseretningslinjer for QST*R-21 Euplex 1. Den negative kontrol må ikke vise skarpe spidser inden for aflæsningsområdet fra 100 til 510 bp. 2. Den positive kontrol skal vise de forventede resultater, og alle spidser skal opfylde nedenstående kriterier. 3. Ved analyse af DNA-prøver skal der observeres mindst 1 spids for hver testet markør. Det acceptable område for markørspidser, der analyseres på 3130 genetic analyzer, er mellem 50 og 6000 relative fluorescensenheder (rfus relative fluorescent units) og for 3500 genetic analyzere mellem 175 og rfus. Spidshøjder, der falder uden for dette område, må ikke analyseres. 4. Elektroforetogrammer af dårlig kvalitet, der skyldes for stor gennemblødning mellem farvestoffarverne (også kaldet pull-up ), eller elektroforetiske spir (skarpe spidser, der forekommer i mere end et farvestof) må ikke fortolkes. PCR-produkterne skal injiceres og analyseres igen. 5. Der foretages analyse ved at vurdere spidsforholdene (A1/A2), hvor A1 er det korteste længdefragments spidsområde, og A2 er det længste længdefragments spidsområde. Det resulterende forhold er diagnostisk for locus-kopinummer. For disomiske kromosomer skal heterozygote markører vise to spidser med lignende højder. Der foretages en komplet analyse af kromosomets kopinummerstatus ved sammenligning med spidsområdeforholdene. 6. Heterozygote dialleliske (dvs. to alleler) markører skal falde inden for et forholdsvindue på 0,8 til 1,4. For to alleler, der er adskilt med mere end 24 bp i størrelse, er et forhold op til 1,5 imidlertid acceptabelt. Enhver værdi, der falder inden for dette område, refereres som havende et forhold på 1:1. Hvis forholdsbalancen falder uden for dette vindue, kan det skyldes flere faktorer som f.eks.: Fuld kromosomtrisomi Delvis kromosomtrisomi (inklusive submikroskopiske duplikationer) Mosaikisme Kontaminering af anden genotype (f.eks. moder, tvilling, eksternt) Stuttere, der forårsager forvrængning Selektiv amplifikation af én allele, der forårsager forvrængning Polymorfismer på primersted Somatiske mikrosatellitmutationer Guide to Interpretation (Fortolkningsvejledningen) giver eksempler på typiske profiler for mange af disse. Homozygote markører er ikke informative, da der ikke kan bestemmes et forhold. 7. For at fortolke et resultat som unormalt (dvs. der forekommer trisomi) kræves mindst to informative markører, der er forenelige med en triallelisk genotype sammen med alle andre markører, der ikke er informative. Det frarådes at fortolke et resultat som unormalt på basis af information fra kun én markør. Trisomi bestemmes af både: ANE21BYDA 002 OKT-2015 Side 13 af 40
14 7.1. To spidser af forskellig højde, der skyldes, at den ene af spidserne repræsenterer to alleler, som er fælles for den ene eller begge forældre. I dette tilfælde klassificeres forholdet mellem de to spidser som 2:1 eller 1:2, således at A1/A2 vil give et resultat i området 1,8 til 2,4, når spidsen, der repræsenterer den korteste allele, er større i område end den spids, der repræsenterer den længste allele, eller hvor A1/A2 vil give et resultat i området 0,45 til 0,65, når spidsen, der repræsenterer den korteste allele, er mindre i område end den spids, der repræsenterer den længste allele Der forekommer tre spidser af sammenlignelig højde. Forholdet mellem spidserne vil være klassificeret som 1:1:1, og deres værdier falder inden for normalområdet på 0,8 1,4 (selvom et alleleforhold på op til 1,5 for alleler, der er adskilt med mere end 24 bp, er acceptabelt). Hvis dette ikke forekommer, kan det skyldes en af de faktorer, der er nævnt i trin For at fortolke et resultat som normalt kræves mindst to informative markører, der er forenelige med en diallelisk genotype sammen med alle andre markører, der ikke er informative. Et normalt resultat angiver det normale komplement af to for de testede kromosomer. 9. Spidsområdeforhold, der falder mellem de normale og unormale områder, klassificeres som utilstrækkelige. Utilstrækkelige resultater kan gøres tilstrækkelige ved at anvende enkelte kromosomsæt. 10. Hvis der opnås både normale og unormale allelemønstre for et enkelt kromosom, anbefales det at foretage opfølgende studier for at identificere årsagen til de afvigende resultater, før der drages eventuelle konklusioner. 11. Allelestørrelsesområder for markører kan i sjældne tilfælde overlappe hinanden. Hvis der er mistanke om dette, kan en analyse med enkeltkromosomsættene løse det. ANE21BYDA 002 OKT-2015 Side 14 af 40
15 Funktionskarakteristika INTERN VALIDERING Tredive (30) DNA-prøver udtaget fra fostervand eller moderkageprøver og med kendt kromosom 21- ploidystatus blev testet med Elucigene QST*R-21 Euplex. Resulterende data blev analyseret under anvendelse af de anbefalede metoder. Alle tredive prøver amplificerede tilfredsstillende ved første forsøg; af disse konstateredes 25 at være normale og 5 tydede på tilstedeværelsen af en trisomi 21. Alle resultater viste sig at være100% samstemmende med resultater, der tidligere var opnået med en alternativ etableret metode. ANE21BYDA 002 OKT-2015 Side 15 af 40
16 Analysevejledning til GeneMapper (v3.7 og nyere) Bemærk: Følgende GeneMapper-screen shots er taget fra GeneMapper v5.0 Importering og analyse af QST*R-filer 1. Åbn GeneMapper-programfilen 2. Klik på for at tilføje datafiler i et nyt projekt Gå derhen, hvor de rå.fsa-datafilter er gemt, fremhæv de ønskede datafiler, og klik på knappen Add to List>>. 3. Kørselsmappen vil nu blive vist i vinduet Samples to add (prøver, der skal tilføjes). Dobbeltklikker man på kørselsmappens ikon i dette vindue vises de fsa-filer, der skal importeres. Prøver tilføjes dernæst ved at klikke på forneden i skærmbilledet. Datafilerne vises nu i hovedskærmbilledet i GeneMapper (figur 2) Figur 2: Prøverne er klar til at føjes til projektet ANE21BYDA 002 OKT-2015 Side 16 af 40
17 Import af QST*R GeneMapper-analyseindstillinger i GeneMapper Manager Det er nødvendigt at importere QST*R-indstillingerne for GeneMapper. Denne proces kontrolleres via grænsefladen GeneMapper Manager. QST*R GeneMapper-indstillinger er tilgængelige fra Gen- Probes hjemmeside: 1. Åbn programmet 'GeneMapper Manager ved at klikke på ikonet. 2. Vælg fanen Analysis Methods, og klik dernæst på importknappen. 3. Gå til og importer den/de nødvendige QST*R-analyseindstillingsfil(er) (3130 eller 3500) 4. Gentag processen, vælg den relevante fane, og importer de tilsvarende filer for: Tabel Settings (tabelindstillinger) Plot Settings (plotindstillinger) Size Standards (størrelsesstandarder) Bemærk: Det er ikke nødvendigt at importere filer til Cluster Plot Settings (gruppeplotindstillinger), Matrices (matricer), SNP Sets (SNP-sæt) og Report Settings (rapportindstillinger). Import af QST*R-21 Euplex-panelindstillinger i Panel Manager Det er nødvendigt at importere QST*R-21 Euplex -panel- og bin-indstillinger til GeneMapper. Denne proces foretages via grænsefladen Panel Manager (panelstyring). QST*R-21 Euplex specifikke GeneMapper-panel- og bin-indstillingsfiler er tilgængelige på Elucigenehjemmesiden: 1. Åbn programmet 'Panel Manager ved at klikke på ikonet. 2. Klik på Panel Manager (panelstyring) på venstre navigationsvindue. Panel Manager (panelstyring) vil nu fremstå markeret med blåt. 3. Vælg File/Import Panels (fil/importer paneler). Gå til og importer GeneMapper-panelfilen QSTR-21 Euplex GeneMapper Panel File.txt (figur 3). 4. Panelfilen vises nu i venstre navigationsvindue. Klik på panelfilen og kontroller, at den fremstår markeret med blåt. 5. Vælg File/Import Bin Set (fil/importer bin-sæt). Gå til og importer GeneMapper-bin-filen QSTR-21 Euplex GeneMapper Bin File.txt (figur 4). 6. Klik på Apply (anvend), og klik derefter på OK. ANE21BYDA 002 OKT-2015 Side 17 af 40
18 Figur 3: Import af QST*R-21 Euplex GeneMapper panelfil Figur 4: Import af QST*R-21 Euplex GeneMapper bin-fil ANE21BYDA 002 OKT-2015 Side 18 af 40
19 Ændring af analyseparameterfilen Det kan være nødvendigt at ændre standardindstillingerne for Analysis Ranges (analyseområder) i QST*R-analyseindstillingerne sådan, at de passer til lokale forhold under kørslen. Minimumsanalyseområdet vil afhænge af de kapillærer og polymer, der anvendes i forbindelse med dataindsamlingen. Få vist de aktuelle analyseindstillinger: 1. Åbn programmet 'GeneMapper Manager ved at klikke på ikonet. 2. Vælg fanen Analysis Methods (analysemetoder). Den importerede QST*R-fil vil stå anført som QSTR Analysis v Klik på QSTR Analysis v02. Linjen vil nu fremstå markeret. 4. Klik på knappen Open (åbn), og vælg fanen Peak Detector (spidsdetektor) (figur 5). Analyseområderne er som standard sat til at starte ved og slutte ved Figur 5: Analyseområder ANE21BYDA 002 OKT-2015 Side 19 af 40
20 Sådan findes det korrekte analyseområde for jeres laboratorium: 1. Dobbeltklik i hovedvinduet i GeneMapper på den importerede kørselsmappe for at se listen over de fsa-filer, der findes i mappen. 2. Vælg en fsa-fil. 3. Klikker man på fanen Raw data (rådata) vises elektroferogrammet med rådata. 4. Brug den første spids i størrelsesstandarden (f.eks. 75 bp af GS500LIZ) som guide, og bestem et datapunkt, der er ca. 100 datapunkter større (figur 6). Dette bestemmer det laveste punkt i det analyserbare område. 5. Sørg for at det maksimale analyseområde omfatter den største spids på størrelsesstandarden (f.eks. 500bp af GS500LIZ eller 600bp af GS600LIZv2). 6. Indlæs de nye værdier i QST*R-analysefilen (der opnås adgang som ovenfor beskrevet). Figur 6: Konstatering af minimumsområdet ved hjælp af prøvens rådata ANE21BYDA 002 OKT-2015 Side 20 af 40
21 Analyse af importerede QST*R-21 Euplex-filer 1. Vælg QST*R Table Settings v02 (figur 7) i hovedvinduet i GeneMapper. Figur 7: Indstilling af QST*R-tabelindstillinger 2. Vælg QSTR Analysis v02 under Analysis Method. Udfyld hver kolonne nedad ved at trykke på 'Ctrl+D'. Gentag denne proces ved at vælge QSTR 21 Euplex til under Panel - overskriften, og QSTR under 'Size Standard'-overskriften. Husk hver gang at udfylde nedad ved at trykke på Ctrl+D for at sikre, at hver indstilling gælder den komplette prøveliste. 3. Klik på for at starte prøveanalysen. Tildel projektnavn, når der bedes om det. Visning af QST*R-21 Euplex-data 1. Marker prøven, der skal analyseres (fremhæv prøverækken). 2. Klik på for at vise plotter ( Display Plots ). 3. Vælg QST*R Plot settings (QST*R-plotindstillinger) (figur 8). Figur 8: Brug rullemenuen til at vælge QST*R-plotindstillingerne. 4. Plotvinduet vil vise prøveprofilen sammen med de tabulerede data (figur 9). GeneMapper mærker automatisk maksimalt to spidser for hver markør. Hvis der findes tre alleler for en markør, skal den tredje umærkede spids mærkes manuelt (se: Manuel redigering af profiler nedenfor). Bemærk: Allelestørrelsesområder for hver markør er baseret på tidligere observerede data. Sjældne alleler kan falde uden for det givne markørstørrelsesområde og det kan blive nødvendigt at justere binsættet tilsvarende. 5. Det anbefales, at plotvinduet har Single click editing (étkliksredigering) aktiveret. Det gøres ved at vælge Alleles/set click editing (alleler/indstil klikredigering) og kontrollere, at denne mulighed er valgt. ANE21BYDA 002 OKT-2015 Side 21 af 40
22 Figur 9: Prøveplotvindue, der viser mærkede spordata og tilsvarende genotypetabel Manuel redigering af profiler ADVARSEL! GeneMapper tildeler kun mærker for op til 2 spidser pr. markør. Det kan derfor blive nødvendigt at redigere profiler manuelt, dvs. ved tildeling af mærker på tredjespidser (hvis de forekommer) eller fjerne mærker fra stutter-spidser. Tilføj et spidsmærke ved at venstreklikke på den umærkede spids. Du vil få mulighed for at tilføje en allelekommentar. Klik på OK. Spidsen vil nu blive mærket med sin størrelse i basepar og sit spidsområde. Tabellen inkorporerer automatisk den netop mærkede spids. Fjern et spidsmærke ved at venstreklikke på spidsmærket. Du vil få mulighed for at slette en allelekommentar. Klik på OK. Spidsmærket fjernes nu. Tabellen fjerner automatisk de slettede spidsdata. Kopiering af tabeldata 1. Fremhæv alle rækker i tabellen i bunden af plotvinduet. 2. Kopier de valgte rækker ved at trykke på tasterne Ctrl+C. ANE21BYDA 002 OKT-2015 Side 22 af 40
23 QST*R-21 Euplex-rapportskabelon Den tilhørende QST*R-21 Euplex-rapportskabelon kan benyttes til at bestemme spidsforholdene for en markør og bidrage til analysen af data. Den specifikke rapportskabelon QST*R-21 Euplex er tilgængelig på hjemmesiden: 1. Åbn QST*R-21 Euplex-rapportskabelonfilen (QSTR-21 Euplex Report Template.xlsm). 2. Hvis rapportskabelonen viser en advarsel, der angiver, at makroer er blevet deaktiveret, skal du klikke på knappen Enable Content (aktiver indhold) (figur 10) for at aktivere makroerne. Figur 10: Aktivering af makrofunktionen i QST*R-21 Euplex-rapportskabelonen 3. Hvis der vises en sikkerhedsadvarsel (som det ses i figur 11), skal du klikke på Yes for at fortsætte. Figur 11: Tilladelse til at bypasse sikkerheden 4. Indsæt de data, der blev kopieret fra GeneMapper-datatabellen (se ovenfor: Copying Data Table ) i cellen øverste til venstre i det skitserede område ved at trykke på Ctrl+V (se figur 12). ANE21BYDA 002 OKT-2015 Side 23 af 40
24 Figur 12: Import af rå GeneMapper-data til QST*R-21 Euplex-rapportskabelonen. 5. De kalkulerede forhold for hver markør vises nu i datatabellen til venstre. Datatabellen kan udskrives eller gemmes som en ny fil for hver enkelt prøve. 6. For at kunne behandle efterfølgende prøver er det vigtigt, at alle data er ryddet helt væk i rapportskabelonen. Dette gøres ved at klikke på knappen 'CLEAR DATA, der findes under rådatatabellen i QST*R-21 Euplex-rapportskabelonen. Nye prøvedata kan nu importeres ved at følge proceduren, der er skitseret ovenfor. ANE21BYDA 002 OKT-2015 Side 24 af 40
25 Scoring af rapporten 1. Trisomi bestemmes af både: a To spidser af forskellig højde, hvilket skyldes, at den ene af spidserne repræsenterer to alleler, som er fælles for begge forældre. I dette tilfælde klassificeres forholdet mellem de to spidser som 2:1 eller 1:2. Hvor A1/A2 vil give et resultat i området 1,8 til 2,4, når spidsen, der repræsenterer den korte allele, er større i område end den spids, der repræsenterer den længste allele, eller hvor A1/A2 vil give et resultat i området 0,45 til 0,65, når spidsen, der repræsenterer den korteste allele, er mindre i område end den spids, der repræsenterer den længste allele. I begge tilfælde vises Ratio (forhold) i kolonnen Warning (advarsel). b Der forekommer tre spidser af sammenlignelig højde. Spidsforholdet vil være klassificeret som 1:1:1, og deres værdier falder inden for normalområdet på 0,8-1,4 (selvom der for alleler, der er adskilt med mere end 24 bp, er et alleleforhold på op til 1,5 acceptabelt). I dette tilfælde vises 3 Alleles (3 alleler) i kolonnen Warning (advarsel). 2. For at fortolke et resultat som unormalt (dvs. der forekommer trisomi) kræves mindst to informative markører, der er forenelige med en triallelisk genotype sammen med alle andre markører, der ikke er informative. Det frarådes at fortolke et resultat som unormalt på basis af information fra kun én markør. 3. For at fortolke et resultat som normalt kræves mindst to informative markører, der er forenelige med en diallelisk genotype sammen med alle andre markører, der ikke er informative. Et normalt resultat angiver det normale komplement af to for de testede kromosomer. 4. Spidsområdeforhold, der falder mellem de normale og unormale områder, klassificeres som utilstrækkelige. Utilstrækkelige resultater kan gøres tilstrækkelige ved at anvende enkle kromosomsæt. 5. Hvis en markør mangler spidsdata vises Absent (mangler) i advarselskolonnen. Denne advarsel ses rutinemæssigt ved fravær af Y-kromosommarkører. ANE21BYDA 002 OKT-2015 Side 25 af 40
26 GeneMarker-analysevejledning Bemærk: Følgende screen shots er taget fra GeneMarker v Tilføjelse af prøvefiler til GeneMarker Åbn GeneMarker-programfilen, og vælg, når der bedes om det, Open Data (åbn data). Boksen Open Data Files (åbn datafiler) vises. Klik på knappen Add (tilføj). Dialogen Open (åbn) vises. Gå til den mappe, der rådatafilerne. indeholder 1. Vælg alle filerne med CTRL+A, eller brug tasten CTRL og/eller SHIFT for at vælge individuelle prøver. 2. Klik på knappen Open (åbn) i dialogboksen Open (åbn). De valgte filer vises i feltet Data File List (datafilliste) (figur 13). Figur 13: Prøverne tilføjet til listen Data File (datafil) Klik på knappen OK i boksen Open Data Files (åbn datafiler), og prøverne overføres til GeneMarker. Softwaren vil derefter automatisk åbne vinduet Raw Data Analysis (analyse af rådata) (figur 14). ANE21BYDA 002 OKT-2015 Side 26 af 40
27 Figur 14: Vinduet Raw Data Analysis (analyse af rådata) Import af QST*R-21 Euplex GeneMarker panelindstillinger Det er nødvendigt at importere QST*R-panelindstillingerne for GeneMarker. Denne proces foretages via grænsefladen Panel Editor (panelredigeringsprogram). QST*R-21 Euplex GeneMarker-panelindstillingsfiler er tilgængelige på Elucigene-hjemmesiden: 1. Åbn Panel Editor (panelredigeringsprogram) på rullemenuen Tools (værktøjer) (figur 15). Figur 15: Valg af Panel Editor (panelredigeringsprogram) ANE21BYDA 002 OKT-2015 Side 27 af 40
28 2. Vælg Import Panels (importer paneler) på rullemenuen File (filer). Figur 16: Import af paneler 3. Gå til og importer panelet QSTR-21 Euplex.xml 4. Gentag den påkrævede proces for andre relevante panelfiler. Behandling af data Når filerne med rådata er blevet uploaded til GeneMarker, er de klar til at blive behandlet. Behandlingstrinnet inkluder anvendelsen af en størrelsesstandard, filtrering af støjspidser og, om ønsket, sammenligning med et kendt allelpanel. GeneMarker kombinerer alle disse trin i ét simpelt værktøj, der kaldes Run Wizard (kørselsguide) (figur 17). Kørselsguiden åbnes ved at klikke på ikonet Run Project (kør projekt) på hovedværktøjslinjen. Run Wizard (kørselsguide) oprettelse af en kørselsskabelon Det er nødvendigt at oprette en kørselsskabelon, første gang denne software anvendes, for at analysere QST*R-21 Euplex-data. Dette gøres via Run Wizard (kørselsguide). 1. Kørselsguiden åbnes ved at klikke på ikonet Run Project (kør projekt) på hovedværktøjslinjen. 2. Tildel et skabelonnavn, f.eks. QSTR-21 Euplex 3. Vælg Panel, Size Standard (størrelsesstandard), Standard Colour (standardfarve) og Analysis Type (analysetype) som vist i figur Klik på Save (gem) for at gemme skabelonen til senere analyser. 5. Klik på Next (næste) for at fortsætte. Figur 17: Run Wizard (kørselsguide) - vinduet Template Selection (valg af skabelon) ANE21BYDA 002 OKT-2015 Side 28 af 40
29 Run Wizard (kørselsguide) Data Process (databehandling) Vinduet Data Process (databehandling) i Run Wizard gør det muligt for brugeren at vælge spidsfiltreringsparametrene. 1. Vælg de relevante analyseindstillinger i vinduet Data Process, som vist i figur Klik på Next for at fortsætte. Bemærk: Analyseområdeindstillingen inden for rådataenes analyseboks vil variere afhængigt af den polymer, der blev anvendt under dataindsamlingen. Brugeren skal vælge en startdatapunktværdi, der omfatter 75 bp størrelsesstandardspidsen. Figur 18: Run Wizard (kørselsguide) - Vinduet Data Process (databehandling) Bemærk: For 3500-data øges Minimum Intensity (min. styrke) til 150. Run Wizard (kørselsguide) Additional Settings (yderligere indstillinger) ANE21BYDA 002 OKT-2015 Side 29 af 40
30 Der er ikke behov for yderligere indstillinger til udførelse af en QST*R-analyse (figur 19). 1. Klik på OK for at fortsætte. Figur 19: Run Wizard (kørselsprogram) Additional Settings (yderligere indstillinger) Boksen Data Processing (databehandling) Når der er klikket på OK i boksen Run Wizard Additional Settings (kørselsguide yderligere indstillinger), vises boksen Data Processing (databehandling) (figur 20). Rådataene behandles og størrelsesbestemmes, hvorefter filtreringsparametrene og det valgte QST*R-panel anvendes. 1. Klik på OK i boksen Data Processing, når analysen er færdig. Figur 20: Boksen Data Processing (databehandling) Hovedanalysevinduet ANE21BYDA 002 OKT-2015 Side 30 af 40
31 Hovedanalysevinduet (figur 21) i GeneMarker har et brugervenligt layout. Dette layout inkluderer: Prøvefillister - ses til venstre på vinduet. Det syntetiske gelbillede - ses øverst på vinduet. Dataelektroferogrammer ses under gelbilledet. En rapporttabel - ses til højre på vinduet. Det er i dette vindue vigtigt at kontrollere at alle de rigtige spidser i hver profil er blevet taget med. 1. Dobbeltklik på hver prøve, en ad gangen, i prøvefiltræet på venstre side af skærmbilledet. Højreklik på eventuelle tvivlsomme spidser, og vælg en af mulighederne i dialogboksen, f.eks. redigér eller slet allel, bekræft eller afkræft alt efter hvad, der måtte være relevant. 2. Vælg Applications (programmer) i hovedanalysevinduets rullemenu øverst i skærmbilledet. Vælg Trisomy Analysis (trisomianalyse). Boksen Trisomy Analysis Settings (indstillinger for trisomianalyse) åbnes derefter (figur 22). Figur 21: Hovedanalysevinduet Figur 22: Boksen Trisomy Analysis Settings (indstillinger for trisomianalyse) ANE21BYDA 002 OKT-2015 Side 31 af 40
32 Boksen Trisomy Analysis Settings (indstillinger for trisomianalyse) I boksen Trisomy Analysis Settings (indstillinger for trisomianalyse) er der to faner: 1. Fanen Analysis (analyse) 2. Fanen Statistics Plot (statistikplot) Fanen Analysis (analyse) Fanen Analysis (analyse) giver mulighed for at indstille tærskler for trisomianalyse. Sørg for, at BPG er valgt i analyseboksen og at følgende indstillinger er vist. Peak Height (spidshøjde) 50: Minimumhøjde på 50 for spidser der skal indlæses (150 hvis 3500-data anvendes). Height Ratio (højdeforhold) 30 %: Maksimal procentdel af hovedspidsen, som den anden spids skal nå, for at to alleler kan identificeres. Quantification by Peak Area (kvantificering efter spidsområde). Shorter Length/Longer Length (korteste længde/længste længde) valgt. Tærsklerne for Trisomy Ratio (trisomiforhold) er 0,80-1,40. Apply Linear Correction (anvend lineær korrektion) fravalgt. Klik på OK. ANE21BYDA 002 OKT-2015 Side 32 af 40
33 Vinduet Trisomy Analysis (trisomianalyse) Vinduet Trisomy Analysis (trisomianalyse) (figur 23) gør det muligt for brugeren at gennemgå QST*Rprøvedataene og vise spidsforholdet for hver markør og få adgang til GeneMarker-rapporten. Der er flere visninger, som hjælper brugeren med at analysere dataene: Prøveliste Elektroferogram Forholdsplot Rapporttabel Figur 23: Vinduet Trisomy Analysis (trisomianalyse) Se GeneMarker-manualen for at få mere detaljerede oplysninger om trisomianalysefunktioner og brugen af dem. ANE21BYDA 002 OKT-2015 Side 33 af 40
34 GeneMarker-rapport GeneMarker indeholder en rapportskabelon, der er kompatibel med Elucigene QST*R-sæt. Få adgang til rapporten ved at klikke på ikonet for Print (udskriv), der er placeret på værktøjslinjen øverst til venstre i vinduet Trisomy Analysis (trisomianalyse). Dette åbner vinduet Trisomy Print Settings (indstillinger for trisomiudskrivning) (figur 24). Vinduet Trisomy Print Settings (indstillinger for trisomiudskrivning) Vinduet Trisomy Print Settings (indstillinger for trisomiudskrivning) viser valgmuligheder for medtagelse og visning af prøvedata i GeneMarker-rapporten. Vælg de valgmuligheder, der er vist i figur 24. Sørg for, at Custom Size Range (brugerdefineret størrelsesområde) er sat til 98 bp (Start) og 510 bp (End) (slut). Figur 24: Vinduet Trisomy Print Settings (indstillinger for trisomiudskrivning) ANE21BYDA 002 OKT-2015 Side 34 af 40
35 Udskriftsvisning af GeneMarker-rapporten Klik på Preview (vis udskrift) for at få vist GeneMarker-rapporten (figur 25). Fra dette vindue kan brugeren få vist og udskrive spidsdata for hver prøve tværs over alle markører på en enkel prøverapport på en eller to sider. Figur 25: GeneMarker-rapport GeneMarker-rapporten omfatter følgende elementer: Rapporthoved: Indeholder oplysninger om analyse, projekt, prøve og parametre. Underskriftsfelt: Dato- og initialfelt til dem, der gennemgår rapporten. Elektroferogram: Sammenlignelig med vinduet Trisomy Analysis (trisomianalyse), viser alle farvestofsfarverne for prøvesporet. Rapporttabel: Viser valgte spids- og markørværdier for den aktuelle prøve. Trisomisøgningerne er gråtonede. Der er en ekstra tjekkolonne til initialer for den, der gennemgår rapporten. Korrigeret forholdsplot: Indeholder hele datasættets plotpunkter for alle markører i farvestofsfarven. Symbolformerne repræsenterer forskellige markører og kan dechifreres fra rækken Symbol i Report Table (rapporttabellen). Symboler, der er udfyldt med gult, repræsenterer den aktuelle prøves datapunkter. Symboler med rød kontur repræsenterer trisomisøgninger. Bemærk: Det korrigerede forholdsplot vises kun på en anden side for hver prøve, når Ratio Plot (forholdsplot) er valgt i boksen Trisomy Print Report Settings (indstillinger for udskrivning af trisomirapport). ANE21BYDA 002 OKT-2015 Side 35 af 40
36 BILAG 1: Farvemærker Markørerne er mærket på følgende måde: Se bilag 2 for at få yderligere oplysninger om STR-markører inklusive størrelsesområder. ANE21BYDA 002 OKT-2015 Side 36 af 40
37 BILAG 2: - Tabel med mærkeplacering, observeret heterozygositet, allelstørrelsesområde Bemærk: NED-farvestoffet, der er anvendt i sættene, identificeres spektralt som et gult farvestof. Det vises konventionelt med sort skrift for tydelighedens skyld. *Observerede heterozygositeter er baseret på et antal alleler, der er observeret med et Elucigene Diagnostics testpanel. Disse tal kan derfor adskille sig fra offentliggjorte data og kan også variere efter den population, der testes. ANE21BYDA 002 OKT-2015 Side 37 af 40
38 BILAG 3: GeneMapper-profil GeneMapper normal hanprofil der viser relative positioner på mærker, der er påvist af QST*R-21 Euplex ANE21BYDA 002 OKT-2015 Side 38 af 40
39 Procedurens begrænsninger Denne test er designet til at påvise specifikke kromosomale trisomier og kønskromosomaneuploidier som beskrevet i brugervejledningen. Den kan ikke påvise strukturelle ændringer, der involverer de testede kromosomer og påviser ikke abnormiteter i andre kromosomer. Mosaicisme for de testede kromosomer påvises muligvis ikke. Et QST*R-21 Euplex-resultat kan kun anvendes direkte på det testede væv og repræsenterer muligvis ikke den føtale karyotype. Modercellekontaminering (MCC Maternal cell contamination) og begrænset placental mosaicisme (CPM confined placental mosaicisme) kan resultere i uoverensstemmelser mellem QST*R-21 Euplex og karyotyperesultaterne. Bemærk: Heterozygositeter af de anvendte markører var udtaget fra et vilkårligt prøvesæt, der var sendt til rutineanalyse fra en overvejende nordeuropæisk kaukasisk population. Eventuelle beregninger, der anvender disse heterozygositeter, vedrører udelukkende den population, som prøverne blev taget fra. Der kan foretages en lille undersøgelse, der anvender lokale prøver, som en del af en valideringsundersøgelse for at etablere heterozygositeter i den population, der skal testes. Det forventes ikke, at populationsvariationen ændrer assayets generelle informativitet væsentligt. Ansvarsfraskrivelse Resultater fra dette diagnostiske assay skal fortolkes sammen med andre laboratoriedata og kliniske data, der er tilgængelige for klinikeren. Disse Elucigene reagenser leveres til in vitro diagnostik. Yderligere detaljer om Elucigene QST*R-produkter er tilgængelige på: ANE21BYDA 002 OKT-2015 Side 39 af 40
40 Referencer 1. CG Antenatal Care: Full Guidelines (Corrected June 2008) UK National Institute for Health and Clinical Excellence. 2. O Connor, C. (2008) Trisomy 21 Causes Down Syndrome. Nature Education 1(1). 3. Mansfield E S. Diagnosis of Down syndrome and other aneuploidies using quantitative polymerase chain reaction and s.mall tandem repeat polymorphisms. Human Molecular Genetics (1): Mann K, Fox SP, Abbs SJ, Yau SC, Scriven PN, Docherty Z, Mackie Ogilvie C. Development and implementation of a new rapid aneuploidy diagnostic service within the UK National Health Service and implications for the future of prenatal diagnosis. The Lancet (9287): Mann K, Donaghue C, Fox SP, Docherty Z, Mackie Ogilvie C. Strategies for the rapid prenatal diagnosis of chromosome aneuploidy. European Journal of Human Genetics : Mackie Ogilvie C, Donaghue C, Fox SP, Docherty Z, Mann K. Rapid prenatal diagnosis of an aneuploidy using Quantitative Fluorescence-PCR (QF-PCR). Journal of Histochemistry and Cytochemistry (3): Deutsch S, Choudhury U, Merla G, Howald C, Sylvan A, Antonarakis SE. Detection of aneuploidies by paralogous sequence quantification. Journal of Medical Genetics : ELUCIGENE og QST*R er varemærker tilhørende Gen-Probe Life Sciences Ltd. GENEMARKER er et varemærke tilhørende SoftGenetics Corporation. GENEMAPPER, GENESCAN, NED, VIC, PET, POP-7, LIZ og HI-DI er varemærker, der tilhører Life Technologies Corporation. Meddelelse til køberen: Begrænset licens Dette produkt sælges i henhold til en kontrakt med Life Technologies Corporation. Ved købet af dette produkt erhverver køberen den ikke-overdragelige ret til udelukkende at bruge den købte mængde af produktet og dets komponenter til human in-vitro-diagnostik, udelukkende til den indikation, der er beskrevet i den medfølgende brugervejledning. Ønskes information om opnåelse af yderligere rettigheder til at bruge dette produkt eller dets komponenter, bedes du kontakte [email protected]. Copyright 2015 Delta Diagnostics (UK) Ltd. ANE21BYDA 002 OKT-2015 Side 40 af 40
Elucigene QST*R -produkter Brugervejledning
 Elucigene QST*R -produkter Brugervejledning Produkt Størrelse Katalogkode Elucigene QST*Rplusv2 50 test AN0PLB2 Elucigene QST*R 50 test AN003B2 Elucigene QST*R-XYv2 50 test AN0XYB2 Elucigene QST*R-13 10
Elucigene QST*R -produkter Brugervejledning Produkt Størrelse Katalogkode Elucigene QST*Rplusv2 50 test AN0PLB2 Elucigene QST*R 50 test AN003B2 Elucigene QST*R-XYv2 50 test AN0XYB2 Elucigene QST*R-13 10
Elucigene CF-EU2v1 Vejledning til analysesoftware
 ` Elucigene CF-EU2v1 Vejledning til analysesoftware Fremstillet af Gen-Probe Life Sciences Ltd. Heron House Oaks Business Park Crewe Road Wythenshawe Manchester M23 9HZ For salgsafdeling, kundeservice
` Elucigene CF-EU2v1 Vejledning til analysesoftware Fremstillet af Gen-Probe Life Sciences Ltd. Heron House Oaks Business Park Crewe Road Wythenshawe Manchester M23 9HZ For salgsafdeling, kundeservice
Test dit eget DNA med PCR
 Test dit eget DNA med PCR Navn: Forsøgsvejledning Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA sekvens,
Test dit eget DNA med PCR Navn: Forsøgsvejledning Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA sekvens,
Test dit eget DNA med PCR
 Test dit eget DNA med PCR Forsøgsvejledning Navn: Side 1 af 7 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA
Test dit eget DNA med PCR Forsøgsvejledning Navn: Side 1 af 7 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA
Test dit eget DNA med PCR
 Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA
Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA
DMX styring med USB-interface
 DMX styring med USB-interface Introduktion...2 DMX bibliotek...3 Programmering af kanaler...7 Sådan skabes et show/en lyssekvens...11 Introduktion DMX LightPlayer er en avanceret men meget brugervenlig
DMX styring med USB-interface Introduktion...2 DMX bibliotek...3 Programmering af kanaler...7 Sådan skabes et show/en lyssekvens...11 Introduktion DMX LightPlayer er en avanceret men meget brugervenlig
Test dit eget DNA med PCR
 Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA-sekvens,
Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA-sekvens,
Setup Guide Do It Now Work Smarter
 Setup Guide Do It Now Work Smarter Best Practice Education +45 4070 3035 [email protected] Indbakke: Fjern læserude og første linje i mails 1. Vælg Vis (View) i Startside menuen 2. Vælg Læserude (Reading
Setup Guide Do It Now Work Smarter Best Practice Education +45 4070 3035 [email protected] Indbakke: Fjern læserude og første linje i mails 1. Vælg Vis (View) i Startside menuen 2. Vælg Læserude (Reading
Huskesedler. Design og automatisering af regneark. Microsoft Excel 2013
 Huskesedler Design og automatisering af regneark Microsoft Excel 2013 Januar 2017 Knord Side 2 Indholdsfortegnelse Ark... 4 Beskyttelse... 6 Diagram... 7 Eksport af data... 8 Fejlretning i formler... 9
Huskesedler Design og automatisering af regneark Microsoft Excel 2013 Januar 2017 Knord Side 2 Indholdsfortegnelse Ark... 4 Beskyttelse... 6 Diagram... 7 Eksport af data... 8 Fejlretning i formler... 9
Test dit eget DNA med PCR
 Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA-sekvens,
Test dit eget DNA med PCR Navn: Forsøgsvejledning Side 1 af 8 Formål med forsøget Formålet med dette forsøg er at undersøge jeres arvemateriale (DNA) for et transposon kaldet Alu. Et transposon er en DNA-sekvens,
Daglig brug af JitBesked 2.0
 Daglig brug af JitBesked 2.0 Indholdsfortegnelse Oprettelse af personer (modtagere)...3 Afsendelse af besked...4 Valg af flere modtagere...5 Valg af flere personer der ligger i rækkefølge...5 Valg af flere
Daglig brug af JitBesked 2.0 Indholdsfortegnelse Oprettelse af personer (modtagere)...3 Afsendelse af besked...4 Valg af flere modtagere...5 Valg af flere personer der ligger i rækkefølge...5 Valg af flere
Skifte til Outlook 2010
 I denne vejledning Microsoft Microsoft Outlook 2010 ser meget anderledes ud end Outlook 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
I denne vejledning Microsoft Microsoft Outlook 2010 ser meget anderledes ud end Outlook 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
Camtasia guide. Redigering af video. Trin for trin guide til redigering af video i Camtasia.
 Camtasia guide Trin for trin guide til redigering af video i Camtasia. Redigering af video Det forventes at læsere af denne guide allerede har Camtasia installeret. 1. Hvis du har valgt at redigere i din
Camtasia guide Trin for trin guide til redigering af video i Camtasia. Redigering af video Det forventes at læsere af denne guide allerede har Camtasia installeret. 1. Hvis du har valgt at redigere i din
Brugervejledning til Avery Wizard for Microsoft Office. Dansk version til www.avery.dk - www.avery.no
 Brugervejledning til Avery Wizard for Microsoft Office Dansk version til www.avery.dk - www.avery.no Indholdsfortegnelse 1. Systemkrav 1. Systemkrav for at anvende Avery Wizard 2. Installering af Wizard
Brugervejledning til Avery Wizard for Microsoft Office Dansk version til www.avery.dk - www.avery.no Indholdsfortegnelse 1. Systemkrav 1. Systemkrav for at anvende Avery Wizard 2. Installering af Wizard
Kom i gang med Course Tool 1.2
 Kom i gang med Course Tool 1.2 Indhold Indledning...2 Pris beregning...2 Anvendelse...2 Open Source...2 Anbefalinger...2 Installation...3 USB-Pen...3 Download Libre Office (Draw)...3 Indstil makrosikkerhed...4
Kom i gang med Course Tool 1.2 Indhold Indledning...2 Pris beregning...2 Anvendelse...2 Open Source...2 Anbefalinger...2 Installation...3 USB-Pen...3 Download Libre Office (Draw)...3 Indstil makrosikkerhed...4
Orddeling. Automatisk orddeling. Manuel orddeling. Word 2010 18 thoremil.dk. Vælg fanebladet [Sidelayout] Vælg [Orddeling] Markér Automatisk orddeling
![Orddeling. Automatisk orddeling. Manuel orddeling. Word 2010 18 thoremil.dk. Vælg fanebladet [Sidelayout] Vælg [Orddeling] Markér Automatisk orddeling Orddeling. Automatisk orddeling. Manuel orddeling. Word 2010 18 thoremil.dk. Vælg fanebladet [Sidelayout] Vælg [Orddeling] Markér Automatisk orddeling](/thumbs/24/3949459.jpg) Orddeling Automatisk orddeling Vælg [Orddeling] Markér Automatisk orddeling Manuel orddeling Vælg [Orddeling] Klik [Manuelt] For hvert ord, som vises, kan der gøres følgende: Accepter det foreslåede orddelingssted
Orddeling Automatisk orddeling Vælg [Orddeling] Markér Automatisk orddeling Manuel orddeling Vælg [Orddeling] Klik [Manuelt] For hvert ord, som vises, kan der gøres følgende: Accepter det foreslåede orddelingssted
Hånd@ Tilretning af importdatafiler
 Hånd@ Tilretning af importdatafiler Tilretning af Import data filer.... 3 Fjerne dubletter... 4 Tilret og tilføj kolonne overskrifter... 9 Hvordan fordeles data fra en kolonne til flere?... 10 Sammenføje
Hånd@ Tilretning af importdatafiler Tilretning af Import data filer.... 3 Fjerne dubletter... 4 Tilret og tilføj kolonne overskrifter... 9 Hvordan fordeles data fra en kolonne til flere?... 10 Sammenføje
DANSK SKOLEDATA APS. Tlf. 86 44 80 99 E-mail [email protected] DSA-Ventelisten
 Indholdsfortegnelse Overordnet beskrivelse af programmets funktioner... 2 Log på... 2 Manuel oprettelse af elev.... 3 Optagelse af elever... 3 1 Gruppering og sortering af elever... 3 2 Udvælg aspiranter...
Indholdsfortegnelse Overordnet beskrivelse af programmets funktioner... 2 Log på... 2 Manuel oprettelse af elev.... 3 Optagelse af elever... 3 1 Gruppering og sortering af elever... 3 2 Udvælg aspiranter...
BRUGERVEJLEDNING FIONA ONLINE
 BRUGERVEJLEDNING FIONA ONLINE Indberetning til Nationalbankens betalingsbalance for erhvervsvirksomheder, forsikrings- og pensionsselskaber samt visse finansielle institutter Statistisk Afdeling Version
BRUGERVEJLEDNING FIONA ONLINE Indberetning til Nationalbankens betalingsbalance for erhvervsvirksomheder, forsikrings- og pensionsselskaber samt visse finansielle institutter Statistisk Afdeling Version
Image Converter. Betjeningsvejledning. Indholdsfortegnelse: Version: 1.1.0.0. Sørg for at læse følgende, før Image Converteren anvendes
 Image Converter Betjeningsvejledning Version: 1.1.0.0 Sørg for at læse følgende, før Image Converteren anvendes Indholdsfortegnelse: Overblik over Image Converter P2 Image Converteringsproces P3 Importér
Image Converter Betjeningsvejledning Version: 1.1.0.0 Sørg for at læse følgende, før Image Converteren anvendes Indholdsfortegnelse: Overblik over Image Converter P2 Image Converteringsproces P3 Importér
Minivejledning Kommuniker, På Tryk2
 Minivejledning Kommuniker, På Tryk2 En mini brugervejledning, der viser de væsentligste funktioner i programmet. 1a Begynd at skrive Åbn programmet på skrivebordet. Dette er det kreative hoved-skrivevindue.
Minivejledning Kommuniker, På Tryk2 En mini brugervejledning, der viser de væsentligste funktioner i programmet. 1a Begynd at skrive Åbn programmet på skrivebordet. Dette er det kreative hoved-skrivevindue.
Manual til hjemmeside i Typo3
 Manual til hjemmeside i Typo3 Gode tips og genvejstaster Ét linieskift Ctrl + A Ctrl + C Ctrl + X Ctrl + V shift + enter (tasten du normalt bruger til linieskift) Markér alt Kopier Klip Sæt ind Oprettelse
Manual til hjemmeside i Typo3 Gode tips og genvejstaster Ét linieskift Ctrl + A Ctrl + C Ctrl + X Ctrl + V shift + enter (tasten du normalt bruger til linieskift) Markér alt Kopier Klip Sæt ind Oprettelse
PCR (Polymerase Chain Reaction): Opkopiering af DNA
 PCR (Polymerase Chain Reaction): Opkopiering af DNA PCR til at opkopiere bestemte DNA-sekvenser i en prøve er nu en af genteknologiens absolut vigtigste værktøjer. Peter Rugbjerg, Biotech Academy PCR (Polymerase
PCR (Polymerase Chain Reaction): Opkopiering af DNA PCR til at opkopiere bestemte DNA-sekvenser i en prøve er nu en af genteknologiens absolut vigtigste værktøjer. Peter Rugbjerg, Biotech Academy PCR (Polymerase
Viditronic NDVR Quick Guide. Ver. 2.0
 Viditronic NDVR Quick Guide Ver. 2.0 1 Indholdsfortegnelse 1. HOVEDMENU 3 1.1 START 5 1.2 AKTIVITETSINDIKATOR: 7 1.3 INFORMATIONS VINDUE: 7 1.4 PTZ KAMERA KONTROL: 7 1.5 SKÆRMMENU 8 1.5.1 AKTIVER BEVÆGELSE:
Viditronic NDVR Quick Guide Ver. 2.0 1 Indholdsfortegnelse 1. HOVEDMENU 3 1.1 START 5 1.2 AKTIVITETSINDIKATOR: 7 1.3 INFORMATIONS VINDUE: 7 1.4 PTZ KAMERA KONTROL: 7 1.5 SKÆRMMENU 8 1.5.1 AKTIVER BEVÆGELSE:
Brugermanual PoP3 og Outlook Office 2003 Webmail www.321mail.dk. Udarbejdet af IT-afdelingen 2005
 Brugermanual PoP3 og Outlook Office 2003 Webmail www.321mail.dk Udarbejdet af IT-afdelingen 2005 Indholdsfortegnelse 1. INDLEDNING... 4 2. OUTLOOK 2003... 4 3. BRUGERVEJLEDNING I BRUGEN AF WEB MAIL...
Brugermanual PoP3 og Outlook Office 2003 Webmail www.321mail.dk Udarbejdet af IT-afdelingen 2005 Indholdsfortegnelse 1. INDLEDNING... 4 2. OUTLOOK 2003... 4 3. BRUGERVEJLEDNING I BRUGEN AF WEB MAIL...
Vester Kopi A/S - Plotservice
 Vester Kopi A/S - Plotservice Vejledning til AutoCad 2000 i forbindelse med plotservice Indhold: Plotter konfiguration i AutoCad 2000 1 Indstillinger i AutoCad 2000 4 Farveplot 6 Plotfiler i AutoCad 2000
Vester Kopi A/S - Plotservice Vejledning til AutoCad 2000 i forbindelse med plotservice Indhold: Plotter konfiguration i AutoCad 2000 1 Indstillinger i AutoCad 2000 4 Farveplot 6 Plotfiler i AutoCad 2000
Individuelle pædagogiske handleplaner for Daginstitution/ Dagpleje. Tabulex Læreplaner
 Individuelle pædagogiske handleplaner for Daginstitution/ Dagpleje Tabulex Læreplaner Indhold IST Individuelle pædagogiske handleplaner... 3 Log på og arbejdsgang... 3 Menupunkt Skabeloner... 4 Beskrivelse
Individuelle pædagogiske handleplaner for Daginstitution/ Dagpleje Tabulex Læreplaner Indhold IST Individuelle pædagogiske handleplaner... 3 Log på og arbejdsgang... 3 Menupunkt Skabeloner... 4 Beskrivelse
Brugervejledning til Kørebog for Pocket PC
 Brugervejledning til Kørebog for Pocket PC Denne vejledning beskriver kort anvendelsen af Kørebog for Pocket PC version 3.0 Programmet giver mulighed for registrering af den daglige kørsel. Registreringen
Brugervejledning til Kørebog for Pocket PC Denne vejledning beskriver kort anvendelsen af Kørebog for Pocket PC version 3.0 Programmet giver mulighed for registrering af den daglige kørsel. Registreringen
TESTPORTAL: BRUGERVEJLEDNING LOG IND ADGANGSKODE
 TESTPORTAL: BRUGERVEJLEDNING LOG IND Testportalen befinder sig på internetadressen http://www.testportal.hogrefe.dk/default.aspx. På denne adresse mødes man af ovenstående skærmbillede. Indtast her dit
TESTPORTAL: BRUGERVEJLEDNING LOG IND Testportalen befinder sig på internetadressen http://www.testportal.hogrefe.dk/default.aspx. På denne adresse mødes man af ovenstående skærmbillede. Indtast her dit
KMD Brugeradministration til Navision og LDV
 KMD Brugeradministration til Navision og LDV Vejledning for Statens Administration og ØSC institutioner. Opdateret 09-09-2015 Indholdsfortegnelse 1 Kom godt i gang... 2 1.1 Login til KMD Brugeradministration...
KMD Brugeradministration til Navision og LDV Vejledning for Statens Administration og ØSC institutioner. Opdateret 09-09-2015 Indholdsfortegnelse 1 Kom godt i gang... 2 1.1 Login til KMD Brugeradministration...
Individuelle pædagogiske handleplaner for Forvaltning. Tabulex Daginstitution Børn
 Individuelle pædagogiske handleplaner for Forvaltning Tabulex Daginstitution Børn Indhold IST Individuelle pædagogiske handleplaner... 3 Log på og arbejdsgang... 3 Skabeloner... 4 Opret skabelon... 5 Stamkort...
Individuelle pædagogiske handleplaner for Forvaltning Tabulex Daginstitution Børn Indhold IST Individuelle pædagogiske handleplaner... 3 Log på og arbejdsgang... 3 Skabeloner... 4 Opret skabelon... 5 Stamkort...
Efter installation af GEM Drive Studio software fra Delta s CD-rom, skal hoved skærmbilledet se således ud: (koden til administrator adgang er: admin)
 Hurtig opstart af Infranor XtrapulsPac-ak drev: Dette er en enkelt og kortfattet vejledning i opsætningen af XtrapulsPac-ak driver til anvendelse i stand-alone mode. Ingen Profibus forbindelse. For senere
Hurtig opstart af Infranor XtrapulsPac-ak drev: Dette er en enkelt og kortfattet vejledning i opsætningen af XtrapulsPac-ak driver til anvendelse i stand-alone mode. Ingen Profibus forbindelse. For senere
Vejledning til udskrivning af etiketter/labels og konvolutter i Blåt Medlem
 Vejledning til udskrivning af etiketter/labels og konvolutter i Blåt Medlem Blåt Medlem giver mulighed for at udskrive etiketter/labels og kuverter til medlemmerne af den enhed man er medlemsansvarlig
Vejledning til udskrivning af etiketter/labels og konvolutter i Blåt Medlem Blåt Medlem giver mulighed for at udskrive etiketter/labels og kuverter til medlemmerne af den enhed man er medlemsansvarlig
Novotek Planning Systems A/S 2013 Version 1.0 Jan 2013 ROB-EX 4.2
 Version 1.0 Jan 2013 ROB-EX 4.2 Indhold Hovedskærmens opbygning... 2 Tastaturgenveje... 3 Hovedskærmbilleder... 4 Stamdata generelt... 5 Kalender... 6 Opret/rediger kalender... 7 Specifik kalender pr.
Version 1.0 Jan 2013 ROB-EX 4.2 Indhold Hovedskærmens opbygning... 2 Tastaturgenveje... 3 Hovedskærmbilleder... 4 Stamdata generelt... 5 Kalender... 6 Opret/rediger kalender... 7 Specifik kalender pr.
Indholdsfortegnelse. EasyIQ IDM 5.4 Brugermanual
 Indholdsfortegnelse Indledning... 2 Forsiden... 2 Dine genveje... 3 Nyheder... 3 EasyIQ og EasyIQ Quick Funktioner... 3 Administration... 8 Licens... 8 Nyheder... 9 Eksterne links... 11 Log... 12 Password...
Indholdsfortegnelse Indledning... 2 Forsiden... 2 Dine genveje... 3 Nyheder... 3 EasyIQ og EasyIQ Quick Funktioner... 3 Administration... 8 Licens... 8 Nyheder... 9 Eksterne links... 11 Log... 12 Password...
KMD Brugeradministration til Navision og LDV
 KMD Brugeradministration til Navision og LDV Vejledning for selvejere. Opdateret 09-09-2015 Indholdsfortegnelse 1 Overordnet liste af funktoner... 2 2 Vejledning... 3 2.1 Login til KMD Brugeradministration...
KMD Brugeradministration til Navision og LDV Vejledning for selvejere. Opdateret 09-09-2015 Indholdsfortegnelse 1 Overordnet liste af funktoner... 2 2 Vejledning... 3 2.1 Login til KMD Brugeradministration...
Easy Guide i GallupPC
 Easy Guide i GallupPC Version. 6.00.00 Gallup A/S Masnedøgade 22-26 DK 2100 København Ø Telefon 39 27 27 27 Fax 39 27 50 80 Indhold SÅDAN KOMMER DU I GANG MED AT ANVENDE GALLUPPC... 2 TILFØJELSE AF UNDERSØGELSER
Easy Guide i GallupPC Version. 6.00.00 Gallup A/S Masnedøgade 22-26 DK 2100 København Ø Telefon 39 27 27 27 Fax 39 27 50 80 Indhold SÅDAN KOMMER DU I GANG MED AT ANVENDE GALLUPPC... 2 TILFØJELSE AF UNDERSØGELSER
IVD Bacterial Test Standard
 Brugsanvisning IVD Bacterial Test Standard Standard for massekalibrering, som viser en typisk Escherichia coli DH5- alfapeptid- og -proteinprofil plus yderligere proteiner. Til anvendelse ved matrix-assisteret-laser-desorption-ionisering
Brugsanvisning IVD Bacterial Test Standard Standard for massekalibrering, som viser en typisk Escherichia coli DH5- alfapeptid- og -proteinprofil plus yderligere proteiner. Til anvendelse ved matrix-assisteret-laser-desorption-ionisering
Instruktioner i installation og afinstallation af Windows PostScript- og PCLprinterdrivere
 Instruktioner i installation og afinstallation af Windows PostScript- og PCLprinterdrivere version 8 Denne fil med vigtige oplysninger indeholder en vejledning til installation af Custom PostScript- og
Instruktioner i installation og afinstallation af Windows PostScript- og PCLprinterdrivere version 8 Denne fil med vigtige oplysninger indeholder en vejledning til installation af Custom PostScript- og
e-konto manual 01.08.2011 e-konto manual Side 1
 e-konto manual 01.08.2011 e-konto manual Side 1 Indhold 1. Overordnet beskrivelse... 3 2. Login... 3 3. Se og ret kundeoplysninger... 4 4. Rediger kontaktoplysninger... 6 5. Skift adgangskode... 7 6. BroBizz-oversigt...
e-konto manual 01.08.2011 e-konto manual Side 1 Indhold 1. Overordnet beskrivelse... 3 2. Login... 3 3. Se og ret kundeoplysninger... 4 4. Rediger kontaktoplysninger... 6 5. Skift adgangskode... 7 6. BroBizz-oversigt...
3 Tilføj printer "HP-GL/2 devices, ADI 4.3 - for Autodesk by HP" 5 Klik "Printer ikonet" - Print/Plot configuration
 Plot filer fra AutoCad 14. 1 Åben Autocad 14 2 Klik "Filer" og vælg "Printer setup" 3 Tilføj printer "HP-GL/2 devices, ADI 4.3 - for Autodesk by HP" 4 Klik "Ok" 5 Klik "Printer ikonet" - Print/Plot configuration
Plot filer fra AutoCad 14. 1 Åben Autocad 14 2 Klik "Filer" og vælg "Printer setup" 3 Tilføj printer "HP-GL/2 devices, ADI 4.3 - for Autodesk by HP" 4 Klik "Ok" 5 Klik "Printer ikonet" - Print/Plot configuration
1.TILBUD NYT TILBUD 1.1 TRIN FORUDSÆTNINGER
 1.TILBUD Fanen Tilbud giver en oversigt over alle de tilbud, der ligger i din database. Det er også herfra, at du har mulighed for at oprette, kopiere eller redigere et eksisterende tilbud. Det følgende
1.TILBUD Fanen Tilbud giver en oversigt over alle de tilbud, der ligger i din database. Det er også herfra, at du har mulighed for at oprette, kopiere eller redigere et eksisterende tilbud. Det følgende
Mini-guide til Retox Databasen er tilgængelig fra klik på linket
 Mini-guide til Retox Databasen er tilgængelig fra www.retox.dk, klik på linket Som udgangspunkt kan alle se arbejdspladsbrugsanvisningerne, hvis man er på regionens netværk. Hvis der skal tilføjes eller
Mini-guide til Retox Databasen er tilgængelig fra www.retox.dk, klik på linket Som udgangspunkt kan alle se arbejdspladsbrugsanvisningerne, hvis man er på regionens netværk. Hvis der skal tilføjes eller
Brug af Discoverer. 1. Start Discoverer ved at klikke på knappen Discoverer på
 Oprette projektark med simpel tabel Brug af Discoverer 1. Start Discoverer ved at klikke på knappen Discoverer på www.kirkeportal.dk 2. Angiv kontonummer, brugernavn og password. Det er det samme som anvendes
Oprette projektark med simpel tabel Brug af Discoverer 1. Start Discoverer ved at klikke på knappen Discoverer på www.kirkeportal.dk 2. Angiv kontonummer, brugernavn og password. Det er det samme som anvendes
5. OPSÆTNING DOKUMENTSKABELONER 5.1 TRIN
 5. OPSÆTNING DOKUMENTSKABELONER Under fanen Dok. skabeloner kan du arbejde med de skabeloner som du har i systemet, eller du kan oprette nye. I denne vejledning kigger vi på hvordan du kan tilrette selve
5. OPSÆTNING DOKUMENTSKABELONER Under fanen Dok. skabeloner kan du arbejde med de skabeloner som du har i systemet, eller du kan oprette nye. I denne vejledning kigger vi på hvordan du kan tilrette selve
Sådan styrer du dine sidetal Word
 Sådan styrer du dine sidetal Word Her vil du kunne finde guides til Word, om hvordan man indsætter sidetal. Der er også et afsnit om hvordan man oprette en automatisk indholdsfortegnelse. Sidetal Word
Sådan styrer du dine sidetal Word Her vil du kunne finde guides til Word, om hvordan man indsætter sidetal. Der er også et afsnit om hvordan man oprette en automatisk indholdsfortegnelse. Sidetal Word
Indhold. Indholdsfortegnelse
 Indholdsfortegnelse Indhold Indledning... 2 Forsiden... 2 Dine genveje... 3 Nyheder... 3 EasyIQ og EasyIQ Quick Funktioner... 3 Administration... 6 Licens... 7 Nyheder... 8 Log... 9 Password... 9 System...
Indholdsfortegnelse Indhold Indledning... 2 Forsiden... 2 Dine genveje... 3 Nyheder... 3 EasyIQ og EasyIQ Quick Funktioner... 3 Administration... 6 Licens... 7 Nyheder... 8 Log... 9 Password... 9 System...
BRUGER KURSUS RAMBØLL HJEMMESIDE
 Til Forsyningsvirksomheder i Danmark Dokumenttype Brugervejledning Rambøll Hjemmeside Full Responsive Dato Oktober 2017 BRUGER KURSUS RAMBØLL HJEMMESIDE BRUGER KURSUS RAMBØLL HJEMMESIDE Revision 01 Dato
Til Forsyningsvirksomheder i Danmark Dokumenttype Brugervejledning Rambøll Hjemmeside Full Responsive Dato Oktober 2017 BRUGER KURSUS RAMBØLL HJEMMESIDE BRUGER KURSUS RAMBØLL HJEMMESIDE Revision 01 Dato
Skifte til OneNote 2010
 I denne vejledning Microsoft Microsoft OneNote 2010 ser meget anderledes ud end OneNote 2007, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
I denne vejledning Microsoft Microsoft OneNote 2010 ser meget anderledes ud end OneNote 2007, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
Manual Serif Web & Tableau Public
 Manual Serif Web & Tableau Public Indhold 2 Start 3 Festivalprogram 4-19 Kursuskatalog 20-22 Dramaskolehold 23-28 Visitkort konsulenter 29-30 Visitkort scener 31-35 Amatørkulturens tal 36-42 VIGTIGT! For
Manual Serif Web & Tableau Public Indhold 2 Start 3 Festivalprogram 4-19 Kursuskatalog 20-22 Dramaskolehold 23-28 Visitkort konsulenter 29-30 Visitkort scener 31-35 Amatørkulturens tal 36-42 VIGTIGT! For
Brugermanual til MOBI:DO Make på Internettet
 Brugermanual til MOBI:DO Make på Internettet Introduktion Med MOBI:DO Make kan du oprette guides, som kan ses i MOBI:DO. En guide virker som en checkliste, der fører brugeren hele vejen igennem en arbejdsopgave.
Brugermanual til MOBI:DO Make på Internettet Introduktion Med MOBI:DO Make kan du oprette guides, som kan ses i MOBI:DO. En guide virker som en checkliste, der fører brugeren hele vejen igennem en arbejdsopgave.
Collect - brugermanual til Y s Men
 Denne vejledning er kun til brug for de personer der har fået adgang til redigering i medlemsdatabasen Collect - brugermanual til Y s Men Indhold Velkommen... 2 Første login... 2 Sådan gemmes nye data...
Denne vejledning er kun til brug for de personer der har fået adgang til redigering i medlemsdatabasen Collect - brugermanual til Y s Men Indhold Velkommen... 2 Første login... 2 Sådan gemmes nye data...
Indholdsfortegnelse. Indholdsfortegnelse.. side 2. Adgang til webgraf 3. Opslag adresse... 4. Styring af layout.. 5. Zoom funktioner..
 Indholdsfortegnelse Indholdsfortegnelse.. side 2 Adgang til webgraf 3 Opslag adresse... 4 Styring af layout.. 5 Zoom funktioner.. 6 Panorere på skærmen. 7 Information om grafikken.... 8-10 Print et udsnit.....
Indholdsfortegnelse Indholdsfortegnelse.. side 2 Adgang til webgraf 3 Opslag adresse... 4 Styring af layout.. 5 Zoom funktioner.. 6 Panorere på skærmen. 7 Information om grafikken.... 8-10 Print et udsnit.....
Brugsanvisning IVD Matrix HCCA-portioned
 Brugsanvisning IVD Matrix HCCA-portioned Rendyrket matrixsubstans til matrix-assisteret-laser-desorption-ionisering time-of-flight-massespektrometri (MALDI-TOF-MS). CARE- produkterne er designet til at
Brugsanvisning IVD Matrix HCCA-portioned Rendyrket matrixsubstans til matrix-assisteret-laser-desorption-ionisering time-of-flight-massespektrometri (MALDI-TOF-MS). CARE- produkterne er designet til at
Daglig brug af Jit-klient
 Daglig brug af Jit-klient Indholdsfortegnelse Opret person...3 Alternativ oprettelse...3 Søgning af personer...4 Send besked...5 Vælg besked...6 Opret mappe...6 Opret skabelon...6 Slet mapper og skabeloner...6
Daglig brug af Jit-klient Indholdsfortegnelse Opret person...3 Alternativ oprettelse...3 Søgning af personer...4 Send besked...5 Vælg besked...6 Opret mappe...6 Opret skabelon...6 Slet mapper og skabeloner...6
Opret CFU-kursusevaluering i Survey Xact
 Printvenlig side for Forsidetekst Opret CFU-kursusevaluering i Survey Xact www.survey-xact.dk Oprettelsen af en kursusevaluering består af flg. trin: 1. Oprettelse af spørgeskema ud fra en skabelon 2.
Printvenlig side for Forsidetekst Opret CFU-kursusevaluering i Survey Xact www.survey-xact.dk Oprettelsen af en kursusevaluering består af flg. trin: 1. Oprettelse af spørgeskema ud fra en skabelon 2.
Quick Guide for Mobil Reception (Omhandler mobil reception også kaldet isymphony)
 Quick Guide for Mobil Reception (Omhandler mobil reception også kaldet isymphony) Generelt Mobil Reception er et værktøj som bruges til at overvåge medarbejdere, kø er og meget andet samt styre dit omstillingsanlæg
Quick Guide for Mobil Reception (Omhandler mobil reception også kaldet isymphony) Generelt Mobil Reception er et værktøj som bruges til at overvåge medarbejdere, kø er og meget andet samt styre dit omstillingsanlæg
Adgang til WebGraf. 1. Start Microsoft Internet Explorer. 2. Skriv: http://kort.ge.dk
 Indholdsfortegnelse Indholdsfortegnelse.. side 2 Adgang til webgraf 3 Opslag adresse... 4 Styring af layout.. 5 Opslag af område via oversigtskort... 6 Zoom funktioner.. 7 Panorere på skærmen. 8 Information
Indholdsfortegnelse Indholdsfortegnelse.. side 2 Adgang til webgraf 3 Opslag adresse... 4 Styring af layout.. 5 Opslag af område via oversigtskort... 6 Zoom funktioner.. 7 Panorere på skærmen. 8 Information
For at gøre det lettere at sende tilbud, har du mulighed for at oprette e-mail skabeloner.
 4. INDSTILLINGER Fanen Indstillinger giver adgang til systemindstillingerne. Som regel skal de kun sættes op én gang for alle, og helst af en person med ansvar for systemopsætningen. Under systemindstillingerne
4. INDSTILLINGER Fanen Indstillinger giver adgang til systemindstillingerne. Som regel skal de kun sættes op én gang for alle, og helst af en person med ansvar for systemopsætningen. Under systemindstillingerne
Kom i gang med... Kapitel 12 Arbejde med skabeloner. OpenOffice.org
 Kom i gang med... Kapitel 12 Arbejde med skabeloner OpenOffice.org Rettigheder Dette dokument er beskyttet af Copyright 2005 til bidragsyderne som er oplistet i afsnittet Forfattere. Du kan distribuere
Kom i gang med... Kapitel 12 Arbejde med skabeloner OpenOffice.org Rettigheder Dette dokument er beskyttet af Copyright 2005 til bidragsyderne som er oplistet i afsnittet Forfattere. Du kan distribuere
Skifte til Excel 2010
 I denne vejledning Microsoft Excel 2010 ser meget anderledes ud end Excel 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre for at få
I denne vejledning Microsoft Excel 2010 ser meget anderledes ud end Excel 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre for at få
Manual til Dynamicweb Februar 2010
 Manual til Dynamicweb Februar 2010 Login... 2 Skabeloner og formater... 3 Filarkivet... 4 Lav en PDF... 5 Opret en ny side... 7 Navngiv siden... 9 Aktiver siden... 9 Sorter sider... 9 Flyt siden... 11
Manual til Dynamicweb Februar 2010 Login... 2 Skabeloner og formater... 3 Filarkivet... 4 Lav en PDF... 5 Opret en ny side... 7 Navngiv siden... 9 Aktiver siden... 9 Sorter sider... 9 Flyt siden... 11
Anvendelse af favoritliste på markedspladsen
 Anvendelse af på markedspladsen Hvad Kommentar Tast Opret på markedspladsen Åben markedspladsen. I venstre side findes r, når du står i fanen Varesøgning Stå i fanen mine, og tryk på Tilføj Tryk på Skriv
Anvendelse af på markedspladsen Hvad Kommentar Tast Opret på markedspladsen Åben markedspladsen. I venstre side findes r, når du står i fanen Varesøgning Stå i fanen mine, og tryk på Tilføj Tryk på Skriv
09/03 2009 Version 1.4 Side 1 af 37
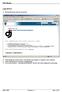 Login til DJAS Gå ind på adressen http://www.djas.dk I feltet Brugernavn skrives den e-mail adresse som brugeren er registeret med i systemet. I feltet Password skrives brugerens adgangskode. Ved at sætte
Login til DJAS Gå ind på adressen http://www.djas.dk I feltet Brugernavn skrives den e-mail adresse som brugeren er registeret med i systemet. I feltet Password skrives brugerens adgangskode. Ved at sætte
Selene brugervejledning
 Selene brugervejledning F2 : Åbner en oversigt med data for det aktive felt. F3: Gemmer data i det aktive vindue Salgsordre : Bruges til oprettelse af Ordre/Arbejdskort/Fakrura Debitor: Debitorregister,
Selene brugervejledning F2 : Åbner en oversigt med data for det aktive felt. F3: Gemmer data i det aktive vindue Salgsordre : Bruges til oprettelse af Ordre/Arbejdskort/Fakrura Debitor: Debitorregister,
LEJERBO.DK INDSÆT BILLEDER, GALLERI OG VIDEO
 1 Indsætte et billede på en side 1. LOG PÅ Log på Mit Lejerbo og gå ind på den lokale side, du skal redigere og klik derefter på Rediger øverst til højre. 2. FIND SIDEN DIT BILLEDE SKAL IND PÅ Klik dig
1 Indsætte et billede på en side 1. LOG PÅ Log på Mit Lejerbo og gå ind på den lokale side, du skal redigere og klik derefter på Rediger øverst til højre. 2. FIND SIDEN DIT BILLEDE SKAL IND PÅ Klik dig
Arkiv i SIMU World. Arkivet ligger i SIMU World, og gør det muligt at arkivere jeres sager direkte i SIMU World.
 Indhold Hvad er Arkivet?... 2 Arkiv er elektronisk, og ligger nederst i hver menu... 3 Arkivgrupper... 3 Oprette hovedmapper under de enkelte faner... 5 Oprette sagsmapper under hovedmapper... 6 Arkivering
Indhold Hvad er Arkivet?... 2 Arkiv er elektronisk, og ligger nederst i hver menu... 3 Arkivgrupper... 3 Oprette hovedmapper under de enkelte faner... 5 Oprette sagsmapper under hovedmapper... 6 Arkivering
Tilpas: Hurtig adgang
 Tilpas: Hurtig adgang Genveje, Se skærmtips Se tips Hold alt tasten nede. Og brug bogstaver Word Fanen Filer PDF dokument Brug skabelon Visninger Husk Luk ved fuldskærmsvisning Brug zoom skyder Marker,
Tilpas: Hurtig adgang Genveje, Se skærmtips Se tips Hold alt tasten nede. Og brug bogstaver Word Fanen Filer PDF dokument Brug skabelon Visninger Husk Luk ved fuldskærmsvisning Brug zoom skyder Marker,
Tabulex Tilsyn - Det pædagogiske tilsyn. Vejledning til tilsynsførende (Forvaltning)
 Tabulex Tilsyn - Det pædagogiske tilsyn Vejledning til tilsynsførende (Forvaltning) Indhold Tilsyn... 3 Om det pædagogiske tilsyn... 3 Log på og arbejdsgang... 4 Skabeloner... 5 Opret skabelon... 6 Navngiv
Tabulex Tilsyn - Det pædagogiske tilsyn Vejledning til tilsynsførende (Forvaltning) Indhold Tilsyn... 3 Om det pædagogiske tilsyn... 3 Log på og arbejdsgang... 4 Skabeloner... 5 Opret skabelon... 6 Navngiv
Pinnacle Studio Titler
 Pinnacle Studio Titler En enkel titel Du kan starte med at oprette en titel, så skal du blot klikke på "T"-ikonet i venstre side af medie vinduet og dine indsatte medieklip vil blive erstattet af et udvalg
Pinnacle Studio Titler En enkel titel Du kan starte med at oprette en titel, så skal du blot klikke på "T"-ikonet i venstre side af medie vinduet og dine indsatte medieklip vil blive erstattet af et udvalg
Prænatal diagnostik Etiske dilemmaer
 Prænatal diagnostik Etiske dilemmaer Eva Hoseth Specialeansvarlig overlæge Ambulatorium for Graviditet og Ultralyd KLINIK KVINDE-BARN OG URINVEJSKIRURGI AALBORG UNIVERSITETSHOSPITAL Retningslinjer for
Prænatal diagnostik Etiske dilemmaer Eva Hoseth Specialeansvarlig overlæge Ambulatorium for Graviditet og Ultralyd KLINIK KVINDE-BARN OG URINVEJSKIRURGI AALBORG UNIVERSITETSHOSPITAL Retningslinjer for
GENEREL FUNKTIONALITET I KMD OPUS ROLLEBASERET INDGANG
 GENEREL FUNKTIONALITET I KMD OPUS ROLLEBASERET INDGANG Arbejdsgang Beskrivelse Handling Overblik over opgaver Du får nu vist Forsiden. Hver fane har en farve, som er unik for den specifikke rolle, og dermed
GENEREL FUNKTIONALITET I KMD OPUS ROLLEBASERET INDGANG Arbejdsgang Beskrivelse Handling Overblik over opgaver Du får nu vist Forsiden. Hver fane har en farve, som er unik for den specifikke rolle, og dermed
Brugervejledning VolvoPentaShop B2C vers.1
 Brugervejledning VolvoPentaShop B2C vers.1 1 - Ordreindtastning 1.1 Samlet ordreproces 1.2 Oprettelse af en quick-ordre 1.3 Opret ordre fra gemte lister 1.4 Opret ordre ved at uploade en fil 1.4.1 Upload
Brugervejledning VolvoPentaShop B2C vers.1 1 - Ordreindtastning 1.1 Samlet ordreproces 1.2 Oprettelse af en quick-ordre 1.3 Opret ordre fra gemte lister 1.4 Opret ordre ved at uploade en fil 1.4.1 Upload
Diginor Brugervejledning
 Diginor Brugervejledning Opret Kunde: Vælg punktet Kunder, Herefter fremkommer billedet til højre. I vindue 1 vil vi få en liste over vores kunder. I vindue 2 vil vi se en liste over kundens biler. 1 kunde
Diginor Brugervejledning Opret Kunde: Vælg punktet Kunder, Herefter fremkommer billedet til højre. I vindue 1 vil vi få en liste over vores kunder. I vindue 2 vil vi se en liste over kundens biler. 1 kunde
SMART Ink 3.0 BRUGERVEJLEDNING FOR MAC OS X-OPERATIVSYSTEMSOFTWARE
 SMART Ink 3.0 BRUGERVEJLEDNING FOR MAC OS X-OPERATIVSYSTEMSOFTWARE Meddelelse om varemærker SMART Ink, SMART Meeting Pro, smarttech, SMART-logoet og alle SMART-sloganer er varemærker eller registrerede
SMART Ink 3.0 BRUGERVEJLEDNING FOR MAC OS X-OPERATIVSYSTEMSOFTWARE Meddelelse om varemærker SMART Ink, SMART Meeting Pro, smarttech, SMART-logoet og alle SMART-sloganer er varemærker eller registrerede
MedWin laboratorieskema
 MedWin laboratorieskema EG Data Inform A/S Albert Ginges Vej 10 9800 Hjørring Dusager 4 8200 Aarhus N Lautrupvang 12 2750 Ballerup Telefon: 96 23 51 00 Telefon Service Desk: 96 23 51 11 - www.egdatainform.dk
MedWin laboratorieskema EG Data Inform A/S Albert Ginges Vej 10 9800 Hjørring Dusager 4 8200 Aarhus N Lautrupvang 12 2750 Ballerup Telefon: 96 23 51 00 Telefon Service Desk: 96 23 51 11 - www.egdatainform.dk
I denne manual kan du finde en hurtig introduktion til hvordan du:
 VORES NORDSJÆLLAND HURTIGT I GANG MANUAL 01: Bruger HVAD INDEHOLDER DENNE MANUAL? I denne manual kan du finde en hurtig introduktion til hvordan du: 1. Finder Vores Nordsjælland hjemmesiden 2. Opretter
VORES NORDSJÆLLAND HURTIGT I GANG MANUAL 01: Bruger HVAD INDEHOLDER DENNE MANUAL? I denne manual kan du finde en hurtig introduktion til hvordan du: 1. Finder Vores Nordsjælland hjemmesiden 2. Opretter
PBX Online Brugervejledning www.pbxonline.dk
 PBX Online Brugervejledning www.pbxonline.dk Indledning PBX Online er dit personlige omstillingsanlæg som ikke kræver noget fysisk udstyr installeret i dit firma. Du styrer det hele via din web browser.
PBX Online Brugervejledning www.pbxonline.dk Indledning PBX Online er dit personlige omstillingsanlæg som ikke kræver noget fysisk udstyr installeret i dit firma. Du styrer det hele via din web browser.
GAPDH PCR modul Manual
 GAPDH PCR modul Manual Katalog nr. 166-5010EDU explorer.bio-rad.com Kopiering kun tilladt til undervisningsbrug Bemærk: Kittet indeholder temperaturfølsomme dele. Åbn derfor straks kassen og læg de pågældende
GAPDH PCR modul Manual Katalog nr. 166-5010EDU explorer.bio-rad.com Kopiering kun tilladt til undervisningsbrug Bemærk: Kittet indeholder temperaturfølsomme dele. Åbn derfor straks kassen og læg de pågældende
Leucosep rør LTK.615 INDLÆGSSEDDEL. Til diagnostisk anvendelse in vitro PI-LT.615-DK-V3
 Leucosep rør LTK.615 INDLÆGSSEDDEL Til diagnostisk anvendelse in vitro PI-LT.615-DK-V3 Vejledende information Tilsigtet anvendelse Leucosep rørene er beregnet til anvendelse i forbindelse med indsamling
Leucosep rør LTK.615 INDLÆGSSEDDEL Til diagnostisk anvendelse in vitro PI-LT.615-DK-V3 Vejledende information Tilsigtet anvendelse Leucosep rørene er beregnet til anvendelse i forbindelse med indsamling
Skifte til PowerPoint 2010
 I denne vejledning Microsoft PowerPoint 2010 ser meget anderledes ud end PowerPoint 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
I denne vejledning Microsoft PowerPoint 2010 ser meget anderledes ud end PowerPoint 2003, og vi har derfor oprettet denne vejledning, så du hurtigere kan komme i gang med at bruge programmet. Læs videre
Mini-guide til Retox Databasen er tilgængelig fra klik på linket
 Mini-guide til Retox Databasen er tilgængelig fra www.retox.dk, klik på linket Som udgangspunkt kan alle se arbejdspladsbrugsanvisningerne, hvis man er på regionens netværk. Hvis der skal tilføjes eller
Mini-guide til Retox Databasen er tilgængelig fra www.retox.dk, klik på linket Som udgangspunkt kan alle se arbejdspladsbrugsanvisningerne, hvis man er på regionens netværk. Hvis der skal tilføjes eller
Oprettelse af Titelblok i Capture og Capture CIS
 e-service Titelblok i OrCAD Capture og Capture CIS Side 1 af 11 Oprettelse af Titelblok i Capture og Capture CIS Note skrevet af : Nordcad Systems Technical Support Revision : April 2003, Release 14.2/9.2.3,
e-service Titelblok i OrCAD Capture og Capture CIS Side 1 af 11 Oprettelse af Titelblok i Capture og Capture CIS Note skrevet af : Nordcad Systems Technical Support Revision : April 2003, Release 14.2/9.2.3,
Avanceret Outlook integration Indholdsfortegnelse
 Indholdsfortegnelse Aktivering af Avanceret Outlook integration... 2 Brugerindstillinger... 2 Brugerindstillinger; journaliseringsdialog... 3 Brugerindstillinger; filtyper der kan journaliseres... 3 Brugerindstillinger;
Indholdsfortegnelse Aktivering af Avanceret Outlook integration... 2 Brugerindstillinger... 2 Brugerindstillinger; journaliseringsdialog... 3 Brugerindstillinger; filtyper der kan journaliseres... 3 Brugerindstillinger;
Sikkerhedskopiering og gendannelse Brugervejledning
 Sikkerhedskopiering og gendannelse Brugervejledning Copyright 2007-2009 Hewlett-Packard Development Company, L.P. Windows er et amerikansk-registreret varemærke tilhørende Microsoft Corporation. Produktbemærkning
Sikkerhedskopiering og gendannelse Brugervejledning Copyright 2007-2009 Hewlett-Packard Development Company, L.P. Windows er et amerikansk-registreret varemærke tilhørende Microsoft Corporation. Produktbemærkning
Vejledning i brug af imastra
 Vejledning i brug af imastra af Daniel Kristian Carlsen 01.06.2010 1 Indholdsfortegnelse 1 Kom i gang... 3 1.1 Åbn imastra... 3 1.2 Skift adgangskode... 3 2 Oprettelse af kryds... 4 2.1 Før vi går i gang...
Vejledning i brug af imastra af Daniel Kristian Carlsen 01.06.2010 1 Indholdsfortegnelse 1 Kom i gang... 3 1.1 Åbn imastra... 3 1.2 Skift adgangskode... 3 2 Oprettelse af kryds... 4 2.1 Før vi går i gang...
Brugeradministrationsvejledning til SMS Web
 Brugeradministrationsvejledning til SMS Web Administration Denne side vil være forskellig afhængig af om man er administrator eller bruger. Administrator får oversigt over alle brugerne samt konfiguration,
Brugeradministrationsvejledning til SMS Web Administration Denne side vil være forskellig afhængig af om man er administrator eller bruger. Administrator får oversigt over alle brugerne samt konfiguration,
